Lecture_structProt - LCQB

Bioinformatique
Structurale
Elodie Laine
Licence de Biologie
Semestre 2, 2016-2017
Computational and Quantitative Biology, UMR 7238, CNRS-UPMC
e-documents: http://www.lcqb.upmc.fr/laine/3V686
e-mail: [email protected]

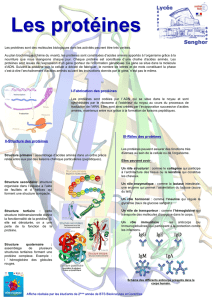
Les protéines: plusieurs dimensions
3V686 –09.03.2016
Les protéines sont des objets
biologiques qui peuvent être
vus/représentés en plusieurs
dimensions.

Les acides aminés
Liaison peptidique
aRginine
lysine (K)
aspartate (D)
glutamate (E)
asparagiNe
glutamine (Q)
Cysteine
Methionine
Histidine
Serine
Threonine
Valine
Leucine
Isoleucine
phenylalanine (F)
tYrosine
tryptophane (W)
Glycine
Alanine
Proline
un acide aminé
•Les acides aminés sont les briques de base
des protéines
•Il en existe 20 types, avec des tailles et
propriétés physico-chimiques différentes
•A l'intérieur des protéines, ils sont connectés
séquentiellement par la liaison peptidique et
appelés "résidus" d'acides aminés
•Chaque résidu contient 10-20 atomes
3V686 –09.03.2016

Les acides aminés
ARG (R)
LYS (K)
ASP (D)
GLU (E)
ASN (N)
GLN (Q)
CYS (C)
MET (M)
HIS (H)
SER (S)
THR (T)
VAL (V)
LEU (L)
ILE (I)
PHE (F)
TYR (Y)
TRP (W)
GLY (G)
ALA (A)
PRO (P)
Les 20 types d'aas sont codés par 3 ou 1 lettre(s)
un acide aminé
3V686 –09.03.2016

…QNCQLRPSGWQCRPTRGDCDLPEFCPGDSSQCPDVSLGDG…
1 protéine = 1 chaîne polypeptidique
~10 à ~1000 résidus
d’acides aminés
1er niveau d’organisation : structure primaire
Liaisons covalentes
Les protéines : plusieurs niveaux d'organisation
3V686 –09.03.2016
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
 24
24
 25
25
 26
26
 27
27
 28
28
 29
29
 30
30
 31
31
 32
32
 33
33
 34
34
1
/
34
100%