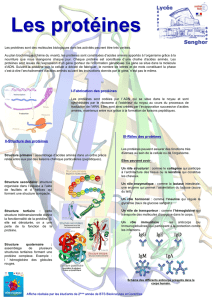
Biologie cellulaire BIO CEL 011 11/01/05 (p.66) L`acide aminé

Biologie cellulaire
BIO CEL 011 11/01/05
(p.66) L’acide aminé adénine rencontre l’ARNt. Une enzyme spécifique intervient à ce
niveau. Ce sont des aminoacides ARNt synthétase. Ces enzymes sont importantes car elles
vont travailler de manière très spécifique. La phénylalanine ARNt synthétase ne concerne que
la phénylalanine par exemple. Quand un acide aminé ARNt synthétase rencontre des acides
aminés ARNt, ils contrôlent ces derniers et peuvent les hydrolyser en cas de non-conformité.
Les ARNm matures : (p.65) Pour la constitution d’une protéine, il y a 20 acides aminés. Il
faut utiliser des codons de 3 bases. Un certain nombre d’acides aminés peuvent être codés par
6 codons. Cela donne beaucoup de possibilités. Il y a donc des redondances dans le code
génétique. La 3ème base est la moins déterminante d’après le tableau du code génétique. Dans
la reconnaissance codon / anti-codon, il y a concordance entre les 1ères et 2nds bases mais on
observe un flottement pour la 3ème. Pour l’alanine, on a GC puis une des 4 bases (p.65 et 67).
L’inosine en position 3’ permet ce flottement car elle peut s’associer à la cytosine, l’adénine
et l’uracile.
La phase d’initiation : (p.68) Association entre un ARNt et eIF2 chez les eucaryotes.
Reconnaissance de la petite sous unité ribosomale au niveau du site P. L’initiateur reconnaît
AUG en 5’ même si les 1ères séquences sont CCACCAUGC. La synthèse se fait par
complémentarité de base. L’ARNt initiateur est situé au niveau de la partie P du ribosome.
La phase d’élongation : (p.69) Le site P libère l’acide aminé formé quand le site A est
investi. Une protéine est synthétisée en commençant par l’acide aminé amino terminal. On a 5
liaisons inter phosphates dont la dernière est utilisée pour s’assurer de la solidité des liaisons
entre les bases. Les systèmes sont assez efficaces. Les erreurs sont inférieures à 1/1000 acides
aminés et cela grâce aux contrôles ainsi que les tests fournis par le délai et par la 5ème liaison
inter phosphate. On a 20 acides aminés ajoutés à la seconde. Les protéines sont synthétisées
en 20 à 60 secondes.
La phase terminal : (p.70) Le codon stop ou facteur de libération eRF se traduit par une
hydrolyse de la liaison du dernier acide aminé et de l’ARNt. Le peptide est libéré et quitte
l’ARNm.
Une protéine est synthétisée par plusieurs ribosomes pour améliorer la vitesse de synthèse. On
appelle cela un polysome (p.70, 2). La conjugaison efficace de la protéine est celle qui a une
configuration thermodynamiquement stable. Cela demande un certain temps pour cette
stabilisation. Il y a des protéines qui permettent d’aider à cette stabilisation des protéines
nouvellement formées. Il y a des protéines de choc thermique (protéines HSP pour Heat
Schock Protein). Ces protéines apparaissent après tout type de chocs. Mais il y a également
des protéines présentent tout le temps en quantité faible mais efficace. Protéines également
appelées chaprons. On les trouve dans toute la cellule. Elles consomment de l’ATP.
L’ubiquitine est une protéine de choc thermique qui s’associe aux histones et aux protéines à
dégrader.

Protéasomes : plusieurs types de protéases qui forment une structure en tonneau. L’ubiquitine
conduit les protéines dans ce tonneau.
Tri des protéines néo synthétisées : (p.72) Le ribosome se fixe sur le réticulum s’il y a un
signal. Sinon il se fixe dans le cytosol (flèches grasses = signal et flèches pointillés = absence
de signal). Les ribosomes dans le cytosol synthétisent des protéines et 3 signaux peuvent faire
entrer dans les mitochondries, le noyau ou les péroxysomes. Pour les ribosomes fixés au
réticulum, la protéine passe sans signal dans le corps de Golgi puis avec des signaux, elle
pourra aller dans des vésicules de sécrétion, l’endolysosome, l’endosome et l’endocytose.
Quand une protéine est dans le cytosol, elle ne fait pas de ponts dissulfures et sa durée de vie
est conditionnée par l’acide aminé N-terminal. Certains acides aminés sont déstabilisants et ils
facilitent l’adjonction d’ubiquitine et donc sa dégradation. L’isoleucine en particulier durée
de vie = 2 minutes ; Arginine = 30 minutes ; Méthionine = 20 heures. Dans le cytosol, des
enzymes enlèvent l’acide aminé N terminal et l’acétylation augmente beaucoup la durée vie
des protéines.
Signal protéine noyau : NLS (Nucléar Localization Signal). L’entrée dans le noyau n’est
pas simple. Rencontre d’une HSP et d’une NLSBP (Blinding Protein) et l’ensemble se
présente au pore nucléaire. Les signaux sont souvent éliminés mais le NLS persiste pour que
les protéines intègrent le noyau en fin de méiose.
Pour atteindre la mitochondrie, la protéine doit traverser la paroi externe et interne. L’HSP 70
maintient les protéines dépliées. A proximité d’un récepteur se fixe un pore et la protéine
s’insère dans le pore avec translocation ATP dépendante. Puis recombinaison d’HSP 70 ou
d’HSP 60 + 10.
On ne sait pas trop comment les protéines entrent dans les péroxysomes mais le procédé est
sûrement proche de celui utilisé pour entrer dans le noyau ou dans les mitochondries.
1
/
2
100%