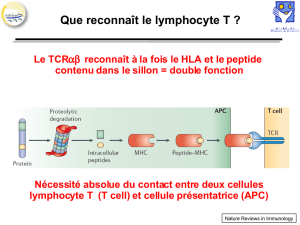
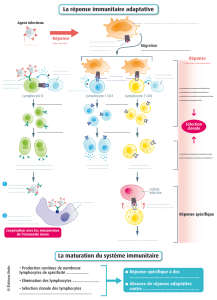
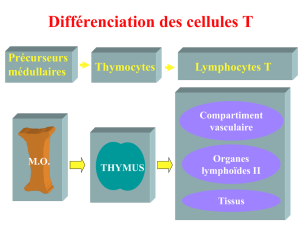
les lymphocytes t - Pôle de Biologie Pathologie Génétique

IMMUNORECEPTEURS
ORIGINE DIFFERENCIATION REPERTOIRE
DES LYMPHOCYTES B et T
MED-2 Professeur Lionel PRIN Immunologie Lille2
Université de Lille –Nord de France

INTRODUCTION
ORIGINE DE LA DIVERSITE DES
RECEPTEURS

IMMUNITE
Apprise
Immunité adaptative
Lymphocyte 2
Lymphocyte 1
Immunité naturelle
Innée
Cellule 2
Cellule 1
Récepteurs invariants
Large spectre d’éléments
reconnus
Récepteurs variables
Reconnaissance = épitope
Récepteurs clonotypiques

épitope ……… paratope
Antigènes Récepteurs de l’immunité adaptative
diversité diversité des domaines
chimique variables
partie : variable constante

domaines
Constants
domaines
Variables
Protéines
associées
1lymphocyte (clone)= 1type de récepteur
" récepteur clonotypique "
Reconnaissance
Activation
Expansion
Différenciation
Apoptose Mémoire
Signal
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
 24
24
 25
25
 26
26
 27
27
 28
28
 29
29
 30
30
 31
31
 32
32
1
/
32
100%