Corrrections TD UEoptionMHM DiagMoMut Carcy

2016/17 DFGSP2
TD UE optionnelle «Maladies
Héréditaire du Métabolisme»
Outils de diagnostic moléculaire
B. CARCY
Réponses aux énoncés

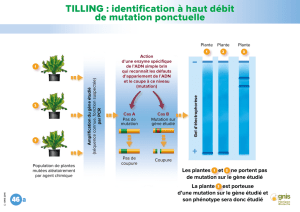
Exercice 1.
A-Dans la cadre d’une recherche de mutation responsable d’une maladie héréditaire du
métabolisme (MHM) au sein d’une famille dont certains membres présentent une déficience
enzymatique caractéristique, le gène (1200pb) codant pour cette enzyme a été amplifié par
PCR (entre les régions 1 et 2) puis séquencé à partir du génome diploïde de 3 hommes (2
sains et un malade). Les résultats du séquençage, dans la région où une différence de profil est
observable entre les 3 individus, sont présentés sur la Figure 1.
Q1 : Sur quel principe repose la méthode de séquençage de Sanger et Coulson qui a été
utilisée ?
1- Terminaison de chaine ADNsb par didésoxyribonucléotide
2- Tous les fragments générés se terminent par un ddNTP
3- On génère autant de fragments d’ADN sb qu’il y a de bases à séquencer et ils
sont tous différents d’une base
4- On détermine l’ordre par électrophorèse (5’=>3’ des plus petits vers les + grands)
Q2 : Quelle est la différence majeure entre cette méthode et celle du pyroséquençage ?
Dans le cas du pyroséquençage, les dNTP sont ajoutés séquentiellement (un à un). C'est
la libération d'un PPi (transformé en ATP par une ATP sulfurylase, lui même étant
transformé en signal lumineux par une luciférase) qui provoquera un flash lumineux.

Q3 : Quelle est la nature de la mutation dans ce gène ?
-Par comparaison homme sain1 (N/N) avec homme malade (M/M) on voit
substitution base A>T en 4ème position. Il s’agit donc d’une microlésion/Mutation
ponctuelle/SNP/RFLP EcoRI (car dans palindrome GAATTC du site EcoRI)
-Confirmé par hétérozygote N/M (sain2) où on observe superposition bases A/T.
Q4 : Quelle serait le mode de transmission de cette maladie ? Peut-elle être de type
récessive lié à l’X ?
-Récessive (car Homme2 est sain mais hétérozygote ) et autosomique car les 2
allèles visibles sur cellule diploide dans hétérozygote.
-Ne peut être lié à l’X sinon on aurait homme sain 2 avec même profil que homme
malade (hémizygote)
B- La séquence des 2 amorces permettant d’amplifier le gène codant pour l’enzyme est la
suivante: 5’-CTATGGCATAGCATCCTATA (sens) et 5'-CCTAAATGCCATCGGTACTA
(antisens).
Q1 : donnez la séquence des 2 extrémités du brin 5'-3' codant sur lesquelles se sont
hybridées ces 2 amorces.
5’----------------------------------------------------------------TAGTACCGATGGCATTTAGG-3’
(amorce R= antisens) ATCATGGCTACCGTAAATCC-5’
5’-CTATGGCATAGCATCCTATA (amorce F= sens)
3’-GATACCGTATCGTAGGATAT-----------------------------------------------------------------5’
=> donc le brin 5'-3' codant est :
5’-CTATGGCATAGCATCCTATA-----------------------TAGTACCGATGGCATTTAGG-3’
Q2 : Donner un programme PCR qui a permis d’amplifier le plus spécifiquement
possible ce gène.
1- Dénaturation : 90°C pd 30s
2- Hybridation :
-La Tm des amorces est calculée selon Tm=4GC+2AT :
opour F => 8X4+12X2=56°C
opour R=> 4X9+11X2= 58°C
-la T° d’hybridation est 5°C < à la + petite Tm soit : 51°C pd 30s
3- Elongation : 72°C pendant 1mn (Taq ADN polymerase)
4- Puis on répète 29X ces 3 étapes=> factuer d’amplification est 2 puissance 30.

C- La digestion enzymatique du fragment PCR par l’enzyme de restriction EcoRI (site de
reconnaissance stricte G/AATTC) scinde l’amplimère de l’individu sain 1 en 2 fragments de
500 et 700pb mais pas celui de l’individu malade.
Q1 : Qu’attendrait-on par ce type d’approche chez l’individu sain 2 ?
3 bandes à 1200/700/500pb
Q2 : Comment appelle-t-on ce type de diagnostic moléculaire ? PCR-RFLP
Exercice 2.
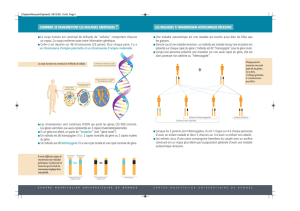
A- Dans le cadre d’une analyse de MHM de transmission récessive liée à l’X, au sein d’une
famille composée d’une fille saine et d’un garçon malade, les résultats de séquençage du
gène responsable de cette maladie à partir du génome diploïde d’une mère (saine) et de sa
fille montrent (dans la région de la mutation) les profils suivants :
Q1 : Citez une MHM qui pourrait correspondre ce type de transmission ?
la maldie de Fabry (déficit en galactosidase A). La mère est porteuse de la mutation mais
non malade (récessive). Elle est donc hétérozygote N/M.
La fille est saine donc homozygote N/N. Le profil de séquençage de la fille est donc la
copie N du gène (11 bases)

Q2 : Interprétez ces profils et déterminez quelle pourrait être la nature de la mutation.
L’analyse des profils de séquençage de la mère (comparée à la fille) suggère sur la copie
M du gène soit un double SNP (A>G et T>A en position 9 et 10, respectivement) soit une
insertion d’une base (G entre les bases G et A des positions 8 et 9) :
Hypothèse 1 (c’est un double SNP en position 9 et 10) : alors l’allèle M
serait AAACCGGGGAT (alors que l’allèle N est AAACCGGGATT,
selon la fille N/N). Ainsi par séquençage des 2 allèles en même temps
(sur diploïde hétérozygote) alors on a :
AAACCGGGGAT (M)
=> AAACCGGG G/A A/T T
AAACCGGGATT (N)
Hypothèse 2 (c’est une insertion d’une base G entre les bases G et A des
positions 8 et 9) : alors l’allèle M serait AAACCGGGGATT (alors que
l’allèle N est AAACCGGGATT, selon la fille N/N). Ainsi par
séquençage des 2 allèles en même temps (sur diploïde hétérozygote, la
mère) alors on a :
AAACCGGGGATT (M)
=> AAACCGGG G/A A/T T/T T
AAACCGGGATT (N)
B- Le profil de séquençage (sur ADN diploïde) chez le garçon malade est le suivant.
Q1- Qu’en concluez-vous quant à la nature de la mutation et sur sa conséquence la plus
probable sur l’expression de l’enzyme?
Chez le garçon malade on ne voit que la copie M (hémizygote car porté par chr X)
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
1
/
13
100%