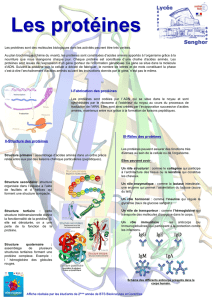
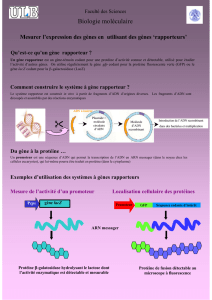
Biochimie

La biochimie du XXIe siècle
En près de 1800 pages abondamment illustrées et en cou-
leurs, la 3e édition française de cet ouvrage livre tous les
secrets découverts à ce jour des biomolécules, des mécanis-
mes d’action des enzymes, du métabolisme, de l’expression
et de la transmission de l’information génétique.
Les nouveautés de la 3e édition
Dans cette nouvelle édition, les auteurs ont ajouté un
grand nombre de notions nouvelles acquises au cours
des huit dernières années, ce qui enrichit presque toutes
les sections.
Parallèlement à ce renouvellement de contenu, ils ont
également revu entièrement l’approche pédagogique,
présentant la matière de manière aussi complète et
précise que possible. Les auteurs ne se contentent pas
d’exposer les connaissances, mais ils attirent l’attention
du lecteur sur la manière dont ces connaissances ont
été acquises. Ils mettent par ailleurs en évidence les
conséquences concrètes des recherches, notamment
leurs applications médicales.
Un référentiel parfaitement à jour
Les professeurs et les chercheurs en biochimie ont entre
leurs mains une référence parfaitement à jour. Quant
aux étudiants en SVT et en sciences médicales, ils peu-
vent non seulement revoir les notions de base, mais
aussi s’initier à la démarche scientifi que et approfondir
des sujets à la pointe de la recherche. Ainsi, à la fi n de
chaque chapitre des exercices et problèmes invitent les
étudiants à la réfl exion.
Traduction de la 4e édition américaine
Lionel Domenjoud est Maître de conférences à
l’Université de Lorraine. Biologiste et embryologiste
moléculaire de formation initiale. Il travaille actuelle-
ment sur les gènes cibles de facteurs de transcription
impliqués dans la cancérogenèse, au sein de l’équipe
de cancérologie STICMo du laboratoire du CRAN de
l’Université de Lorraine.
Pour une compréhension claire des principes
de biochimie et de biologie moléculaire en
relation avec la médecine moderne
Un ouvrage clair et actualisé
Claire, concise et illustrée tout en couleur, la
Biochimie
de Harper
, n’a pas son équivalent pour clarifier le lien
entre la biochimie et les bases moléculaires des ma-
ladies. En combinant d’excellentes illustrations en
couleur à un exposé intégré des maladies biochimiques
et des données cliniques, cette édition présente une
organisation et un équilibre harmonieux de détails et de
concision qui fait défaut à tous les autres ouvrages trai-
tant de ce sujet.
Les nouveautés de cette 5eédition française
uDes nouveaux chapitres sur le vieillissement, le cancer
et la chimie clinique.
uChaque chapitre a été mis à jour pour rendre compte
des derniers progrès des connaissances et de la tech-
nologie.
uChaque chapitre débute à présent par une liste des
objectifs, suivie d’un bref exposé sur l’importance
biomédicale des sujets traités dans le chapitre.
u250 questions à choix multiples pour tester vos con-
naissances et votre compréhension.
uUn nombre accru de tableaux, qui résument les infor-
mations importantes, comme par exemple les besoins
en vitamines ou en sels minéraux.
Traduction de la 29eédition américaine
Lionel Domenjoud est Maître de conférences à l’Université
de Nancy 1, traducteur des ouvrages
Biochimie
(Voet),
Précis
de génomique
(Gibson) et
Principes de génie génétique
(Primrose) pour les éditions De Boeck Supérieur.
Biochimie
de Harper
Murray
I
Bender
I
Botham
Kennelly
I
Rodwell
I
Weil
Biochimie de Harper
Murray
I
Bender
I
Botham
Kennelly
I
Rodwell
I
Weil
aPlus de 600 illustrations en couleur
aUne liste des objectifs au début de chaque chapitre
aDes focus qui font le lien entre le sujet étudié et
l’application biomédicale
a250 questions à choix multiples
aUn résumé et des références bibliographiques
à la fin de chaque chapitre
aUne liste actuelle des sites internet de biochimie
ISBN : 978-2-8041-7561-0
image : D.R.
HARPER
Murray
I
Bender
I
Botham
Kennelly
I
Rodwell
I
Weil
Biochimie de Harper
Conception graphique : Primo&Primo
www.deboeck.com
5eédition
Traduction de Lionel Domenjoud
Murray_2013_Biochimie de Harper 17/04/13 11:20 Page1
L’essentiel de la biochimie
Cette nouvelle édition couvre de façon simple et synthé-
tique les notions de biochimie fondamentales abordées
au cours des études du premier cycle universitaire.
- Après avoir abordé les notions de chimie de base néces-
saires à la compréhension des réactions biochimiques, la
première partie présente ensuite les biomolécules, leur
nature polymérique et leurs fonctions biologiques.
- La deuxième partie concerne les grandes fonctions
métaboliques et les réactions impliquées.
- La troisième partie aborde les trois thèmes de base de la
biologie moléculaire d’un point de vue biochimique,
à savoir : la réplication et la réparation de l’ADN, sa
transcription en ARN puis sa traduction en protéine.
Son approche progressive et enrichie d’exemples pratiques
permet à l’étudiant de mieux intégrer les processus
biochimiques.
L’ouvrage réserve une place importante aux dernières
recherches et applications en biochimie : l’acidification
des océans, l’empreinte ADN, le pyroséquençage de
l’ADN, le processus de développement des médicaments.
Des outils d’entrainement et de révision
Chaque chapitre se termine par une série d’exercices
corrigés. De nombreux exercices sont des études de cas
basées sur des données de publications scientifiques ou
sur des rapports médicaux. Les séries d’exercices peuvent
ainsi servir au travail en classe ou être proposées pour
un devoir à la maison.
Les résumés et glossaires à la fin de chaque chapitre
aident le lecteur à extraire l’essentiel et à contrôler
l’acquisition des notions développées.
Pour aider les étudiants à utiliser le texte comme livre
de référence, chaque partie de chapitre commence
par une série de Concepts Fondamentaux et se termine
par une Révision des Concepts, pour l’autoévaluation.
Cet ouvrage est destiné aux étudiants en 1er cycle de
biochimie et de biologie, aux étudiants en sciences médi-
cales, et à ceux préparant les concours de l’enseignement
(Capes en particulier).
Traduction de la 2eédition américaine
Lionel Domenjoud est Maître de conférences à
l’Université de Nancy 1. Biologiste et embryologiste
moléculaire de formation, il a également traduit les
ouvrages
Biochimie
(Voet),
Biochimie de Harper, Précis
de génomique
(Gibson) et
Principes de génie génétique
(Primrose) pour les éditions De Boeck.
aPlus de 1 000 exercices
aDes exercices Projets bioinformatiques sont destinés à
familiariser les étudiants avec les bases de données en
ligne et les outils logiciels de la bioinformatique.
aLes encadrés Aspects médicaux présentent une description
détaillée de certaines maladies avec leur base biochimique,
leurs symptômes et leur traitement.
aUne liste annotée de références bibliographiques à la suite
de chaque chapitre inclut des articles courts récents.
Biochimie
Pratt
I
Cornely
Pratt
I
Cornely
Biochimie
Pratt
I
Cornely
Biochimie
Traduction de Lionel Domenjoud
9 782804 165741
ISBN : 978-2-8041-6574-1
PRATT
Conception graphique : Primo&Primo
illu : © Alexandr Mitiuc
www.deboeck.com
Pratt_PRATT 10/10/11 12:43 Page1
Chez le même éditeur
Voet
I
Voet
Voet I Voet
Biochimie
Biochimie
Biochimie
Voet I Voet
a Ouvrage mondialement reconnu
a Illustrations interactives
a Guide d’exploration
a Exercices interactifs
a Résumé des concepts à la fi n du chapitre
a Nombreux problèmes
9782804 171018
ISBN : 978-2-8041-7101-8
Conception graphique : Primo&Primo®
illu : © Polina Shuvaeva
VOET
http://noto.deboeck.com : la version numérique de votre ouvrage
• 24h/24, 7 jours/7
• O ine ou online, enregistrement synchronisé
• Sur PC et tablette
• Personnalisation et partage
Traduction de Lionel Domenjoud
3e édition
www.deboecksuperieur.com


Biochimie

Chez le même éditeur
ATKINS P.W. et JONES L., Principes de chimie, 3e éd.
BURROWS A., HOLMAN J., PARSONS A., PILLING G., PRICE G., Chimie3. Introduction à la chimie inorganique,
à la chimie organique et à la chimie-physique
CLAYDEN J., GREEVES N., WARREN S., Chimie organique, 2e éd.
DEPOVERE P., Chimie générale, 3e éd.
DEPOVERE P., Chimie organique, 2e éd.
KARP G., Biologie cellulaire et moléculaire. Concepts et expériences
LODISH H., AMON A., BERK A., BRETSCHER A., KAISER C.A., KRIEGER M., PLOEGH H., SCOTT M.P.,
Biologie moléculaire de la cellule, 4e éd.
MCQUARRIE D.A., GALLOGLY E.B., ROCK P.A., Chimie générale, 3e éd.
MOUSSARD C., Biochimie structurale et métabolique, 3e éd.
MOUSSARD C., Biologie moléculaire. Biochimie des communications cellulaires
MURRAY R.K., BENDER D.A., BOTHAM K.M., KENNELLY P.J., RODWELL V.W., WEIL A., Biochimie de Harper,
5eéd.
PRATT C.W., CORNELY K., Biochimie
PRESCOTT L.M., WILLEY J.M., SHERWOOD L.M., WOOLVERTON C.J., Microbiologie, 4e éd.
SHERWOOD L. Physiologie humaine, 3e éd.
VOLLHARDT K.P.C., SCHORE N.E., Traité de chimie organique, 6e éd.

Biochimie
3e édition
Traduction de la 4e édition américaine de Lionel Domenjoud
VOET VOET
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
 24
24
 25
25
 26
26
 27
27
 28
28
 29
29
 30
30
 31
31
 32
32
 33
33
 34
34
 35
35
 36
36
 37
37
 38
38
 39
39
 40
40
 41
41
 42
42
 43
43
 44
44
 45
45
 46
46
 47
47
 48
48
 49
49
 50
50
 51
51
 52
52
 53
53
 54
54
 55
55
 56
56
 57
57
 58
58
 59
59
 60
60
 61
61
 62
62
 63
63
 64
64
 65
65
 66
66
 67
67
 68
68
 69
69
 70
70
 71
71
 72
72
 73
73
 74
74
 75
75
 76
76
 77
77
 78
78
 79
79
 80
80
 81
81
 82
82
 83
83
 84
84
 85
85
 86
86
 87
87
 88
88
 89
89
 90
90
 91
91
 92
92
 93
93
 94
94
 95
95
 96
96
 97
97
 98
98
 99
99
 100
100
 101
101
 102
102
 103
103
 104
104
 105
105
 106
106
 107
107
 108
108
 109
109
 110
110
 111
111
 112
112
 113
113
 114
114
 115
115
 116
116
 117
117
 118
118
 119
119
 120
120
 121
121
 122
122
 123
123
 124
124
 125
125
 126
126
 127
127
 128
128
 129
129
 130
130
 131
131
 132
132
1
/
132
100%