imagerie génétique : défis computationnels et implémentation gros

IMAGERIE GÉNÉTIQUE :
DÉFIS COMPUTATIONNELS ET
IMPLÉMENTATION GROS
GRAINS SUR CLUSTER
28 JUIN 2012
Forum TERATEC | Vincent Frouin
Déluge de données S Laguitton (CATI-CEA)
B daMota (INRIA-CEA)
28 JUIN 2012 | PAGE 1
CEA | 28 JUIN 2012

NEUROIMAGERIE-GÉNÉTIQUE :
CONTEXTE
28 JUIN 2012
| PAGE 2
CEA | 28 JUIN 2012

NEUROIMAGERIE-GÉNÉTIQUE : MOTIVATIONS
28 JUIN 2012 | PAGE 3
TERATEC 2012 – Déluges de données | 28 JUIN 2012
A R Hariri et al. Science 2002;297:400-403
Etude de groupe, basée sur le génotype
L’étude inclut ~30 sujets
2 groupes : 5-HTT muté vs 5-HTT
Activité plus grande dans l’amygdale à droite (structure impliquée dans le
comportement lié à la peur),

NEUROIMAGERIE-GÉNÉTIQUE : MOTIVATIONS (2)
28 JUIN 2012 | PAGE 4
TERATEC 2012 – Déluges de données | 28 JUIN 2012
sMRI dMRI
fMRI
Patient file, Behavior,
Environment SNPs,CNVs, CGH
Expression, Methylation
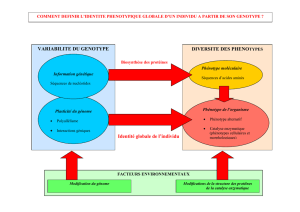
Un outil pour trouver de nouveaux biomarqueurs (via l’endo-phénotype d’imagerie)
Un outil pour étudier des questions de recherche appliquée ou fondamentale
Integration des mesures obtenues à des échelles différentes
Révelateur des réseaux moléculaires ou fonctionnels à l’oeuvre

SOMMAIRE
Neuroimagerie Génétique
Le contexte, les mesures,
L’integration des données produites par des outils de neuroimagerie et de génomique
matures.
Implémentation “gros-grain” du modèle de dosage
allélique
Besoins de run multiples d’un code données (permutation, validation-croisée)
MapReduce pattern, Soma-Workflow
Cluster avec 240 cores
28 JUIN 2012 | PAGE 5
TERATEC 2012 – Déluges de données | 28 JUIN 2012
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
 24
24
 25
25
 26
26
 27
27
 28
28
 29
29
1
/
29
100%