Evolution Moléculaire et Phylogénie

1
Evolution Moléculaire et
Phylogénie
Dominique Mouchiroud
dominique.[email protected]
Biométrie et Biologie Evolutive, UMR5558, Lyon I
Bioinformatique et Génomique Evolutive
Plan du cours
I. L’évolution moléculaire
I1. Le cadre théorique
I2. Les données et les questionnements
II. Evolution de quelques traits moléculaires
II.1 Composition en Base des Génomes
II.2 Taux d’évolution
II.3. Taille des génomes
III. Conclusion
Etude des processus évolutifs en relation
avec les composantes écologiques
Taille des populations
Génome nucléaire et cytoplasmique
Ecologie évolutive
Taille des génomes
Composition en base
Répartition des ETs
Taux d’évolution
Packaging de l
’
ADN
Génomique évolutive Durée de génération
Activité métabolique
Longévité
Masse corporelle
Mode de vie
Dérive génétique
Composante adaptative
Packaging
de
l ADN
……
Traits Moléculaires
Système de reproduction
Traits d’Histoire de Vie
Evolution morphologique
Fossiles vivants ou organismes panchroniques
Coelacanthe
Ornithorynque
Gingko biloba Nautile

2
Le taux d’évolution des génomes
Taux de mutation ou polymorphisme ou diversité génétique
(
intra s
p
écifi
q
ue
)
:
(pq)
Nbre de changements/site/génération
Mesuré entre individu d’une même population
Taux de divergence (inter spécifique) :
Nbre de substitution/site/temps de divergence
Mesuré entre individu d’espèces différentes
Hypothèse neutre (absence de processus sélectif ou non sélectif)
:
Hypothèse
neutre
(absence
de
processus
sélectif
ou
non
sélectif)
:
- taux de divergence = taux de mutation
Vrai si Ne faible(dérive génétique) et coefficient de sélection des
variants proche de zéro
La notion d’horloge moléculaire
• « Le taux de divergence en acides aminés est
approximativement proportionnel au temps de
diver
g
ence
p
aléontolo
g
i
q
ue. »
gp gq
Zuckerkandl and Pauling 62-65
Super protéine ( hémoglobine,
cytochrome c, et fibrinopeptide
A) comparée entre différents
groupes de mammifères. La
ligne en pointillé représente une
estimation de l’horloge
moléculaire. (modifié à partir de
Langley and Fitch 1974)
Variabilité des taux d’évolution
Différence de longueurs de branches est un indicateur de variation de taux d’évolution
Importance de la détection de
l’évolution neutre
– Datation des évènements de spéciation ou de duplication,
– Identification des évènements démographiques (goulots
d’étranglement),
– Recherche de régions sous pression de sélection (éléments
fonctionnels),
–
…..

3
Marqueurs moléculaires neutres
• Pseudogènes : gènes non fonctionnels
• Régions non codantes : intergénique, intron
• Eléments répétées
• Sites synonymes des codons : ne modifient
pas la nature de l’AA codé
•
Région de contrôle de l
’
ADN mitochondrial
Région
de
contrôle
de
l ADN
mitochondrial
Détection sélection avec gène codant
Divergence non synonyme versus Divergence synonyme
ω> 1 d’où DN> DS : sélection adaptative
ω= 1 d’où DN= DS: évolution neutre
ω < 1 d’où DN< DS: sélection purificatrice
DN
DS
ω=
Vrai si la sélection peut jouer (Ne élevée et/ou S élevé )
Si Ne est faible (ex mammifère), la fixation par dérive génétique de mutations
non synonymes faiblement délétaires ou avantageuses est fréquente.
Ceci induit une augmentation du rapport Dn/DS(similaire à la sélection positive).
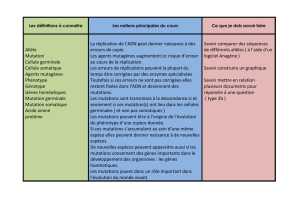
II.2. Taux d’évolution
II. 2.1. Nature et quantification des mutations
II.2.3. Variabilité du taux d’évolution
Les mutations : types
- substitutions (transitions A↔G, T↔C, transversions )
insertions délétions
-
insertions
,
délétions
- duplication de gènes, translocation
- duplication génomique (aneuploïdie, euploïdie)
- transferts horizontaux (gènes, éléments transposables)
- remaniements chromosomiques (fission, fusion, inversion)
Mutagénèse à grande échelle
3.5 milliards d’année d’évolution

4
•Mutations spontanées (facteurs endogènes)
– Susceptibilité de certains nucléotides (C en T pour les CpG,
déamination des c
y
tosines méth
y
lées
),
Dynamique des mutations
yy),
Les CpG et la méthylation
Les génomes de Vertébrés présentent un niveau de méthylation élevé et
spécifique des dinucléotides CG (CpG).
La méthylation est un ajout enzymatique d'un groupement méthyl (CH3) sur une
cytosine.
70-90 % des CpG sont méthylés
NCH
CH
N
C
O
sugar
C
NH 2
methylation deami
NC
CH
N
C
O
sugar
CH3
C
NH 2
5methyl cytosinecytosine
ADN- méthyltransférase
Instabilité évolutive des CpG : taux de mutation 10 X plus important sur les CpG.
Les CpG et la méthylation
Instabilité évolutive des CpG : taux de mutation 10 X plus important sur les CpG.
La déamination de la cytosine est 140 fois plus élevée lorsque l ’ADN
est simple brin (Frederico, 90)
NCH
CH
N
C
O
sugar
C
NH 2
methylation deamination
NC
CH
N
C
O
sugar
CH3
C
NH 2
5methyl cytosinecytosine thymine
NH C
CH
N
C
O
sugar
CH3
C
O
5’-A-T- C-G-G-C-3’
3’-T-A- G-C-C-G-5’
methyl
methyl
5’-A-T- T-G -G-C-3’
3’-T-A-A-C-C-G-5’
5’-A-T- C-A-G-C-3’
3’-T-A-G-T-C-G-5’
30 % des maladies dues à des mutations ponctuelles
(Cooper et al., 1993)
disparition des CpG durant l’évolution des vertébrés
spontanée
Methylation
Evolution de la méthylation
0.25 0.50 0.75 0.95 1.00
Methylation
CpGo/e
G. gallus
M. musculus
H. sapiens
D. rerio A. thaliana D. melanogaster C. elegans
Il existe une corrélation forte entre le degré de méthylation
d’un génome et le taux d’érosion des CpG

5
Les îlots CpG: des structures atypiques
(Bird, 1986)
-régions génomiques de 200 à 5000 pb non-méthylés dans la plupart des tissus
- régions génomiques avec une fréquence en CpG proche de la fréquence
attendue selon la composition en bases G+C (CpGo/e ≈ 1)
- régions génomiques avec une fréquence en bases G+C élevée > 60%)
80
70
60
entage G+C
1,0
0,5
ort CpGo/e
50
40
pourc
rapp
5’ 3’
5’ 3’
start no-start
•Mutations spontanées (facteurs endogènes)
– Susceptibilité de certains nucléotides (C en T pour les CpG, déamination des
cytosines méthylées),
Erreurs de la machinerie cellulaire : copie de l
’
ADN (SNP) slippage ou
Dynamique des mutations
–
Erreurs
de
la
machinerie
cellulaire
:
copie
de
l ADN
(SNP)
,
slippage
ou
recombinaison inégale avec les séquences répétées (CNV), remaniement
chromosomique.
•Mutations induites (facteurs endogènes et exogènes)
– Action d'agents mutagènes (radiations, mutagènes chimiques, produits liés au
métabolisme cellulaire (ROS), pression environnementale,...)
– Activité de parasites intragénomiques
• Rétrovirus: virus intégrant son propre génome dans le génome de son hôte
• Eléments transposables (44% chez l’homme) : éléments capables de se dupliquer et de
se déplacer dans les génomes
• Efficacité de la machinerie de réparation de l’ADN
Taux de mutation chez l’homme
• Chaque individu est porteur d'environ 120 à 180 mutations nouvelles (i.e. qui
n'existaient pas dans les génomes de ses parents),
• La plupart des maladies génétiques humaines répertoriées à ce jour sont la
conséquence de mutations ponctuelles (dans des régions régulatrices ou
codantes),
• Les évènements de duplication/délétion font que les génomes de 2 individus
présentent en moyenne 24 à 70 Mb de différence (1% à 2%) ainsi le répertoire
génique de 2 individus: ± 200 à 600 gènes pour 20 à 23 000 gènes codants !
• Le taux de mutation dans les cellules somatiques est 17X celui des cellules
germinales chez l’homme (Lynch M, 2010, Trends in Genetics)
– Somatique : 10-9 par site et par mitose
–
Germinale:00610
-9
par site et par méiose
Germinale
:
0
,
06
10
par
site
et
par
méiose
dbSNP : http://www.ncbi.nlm.nih.gov/SNP 11 millions SNPs (2008)
HapMap (http://www.hapmap.org) 3,5 millions SNPs humain
Projet 1000 génome
• Les taux de mutation observés résultent d’un
compromis entre le coût des mutations (fardeau
mutationnel) et le coût de la réparation des mutations.
• Les taux de mutation varient au cours du temps au
sein d’un individu, entre types cellulaires, entre
lignées.
• Les taux de divergence observés résultent d’un
compromis entre la taille des populations (mode de
reproduction) et la valeur sélective des mutations.
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
1
/
14
100%