activité en pdf

ActivitéActivité Comment identifier des allèles mutés
à l'aide d'enzymes de restriction
?
I
1 2 3 4
II
1 2 3 4
III
1 2 3
Etablir un diagnostic prénatal pour l'enfant de l'individu III1 dont le frère (III3) et la soeur (III2)
sont atteints d’albinisme oculo-cutané (pas d'albinisme connu dans l'arbre généalogique de son conjoint).
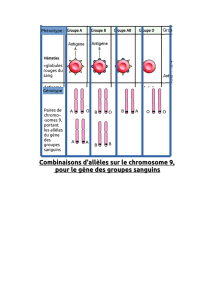
1. La transmission de l'albinisme oculo-cutané
Indices phénotypiques (phénotype clinique ou macroscopique) L'albinisme oculo-cutané est une ano-
malie génétique se manifestant par un déficit de pigmentation de la peau, des poils, de l'iris, de la rétine et
un certain nombre de troubles de la vision.
Cause C'est une déficience de la production d'un pigment sombre, la mélanine, due à l'absence d'une en-
zyme, la tyrosinase . Celle-ci est responsable de 4 réactions de la transformation de
précurseurs en mélanine. Le gène de cette enzyme, situé sur le chromosome 11, présente une certaine va-
riabilité. On connaît:
ê 2 allèles conduisant à des enzymes fonctionnelles (brins non transcrits
nommés “tyrcod1” et “tyrcod2” dans la banque de données du logiciel)
de nombreuses mutations conduisant à des polypeptides non fonctionnels
(”tyralb-a1, a2, ..., a5, b1, ts” dans la banque de données)
(phénotype cellulaire)
ê
Dans ce cas, montrer, rapidement et par simple observation de l'arbre, que le gène est pro-
bablement porté par un autosome et que les allèles mutés déficients ne s'expriment que présents en
double exemplaire (”récessivité” de ces allèles).
Evaluer le risque d'albinisme de l'enfant à naître sachant que la fréquence des hétérozygo-
tes dans la population est voisine de 1%.
1
+Problème à résoudre
page 1
Homme sain
Homme albinos
Femme albinos
Femme saine
On supposera (hypothèse initiale) que les phénotypes alternatifs ne sont liés qu’à un seul gène,
dont on connaît un certain nombre de variants.
phénotypes
moléculaires
alternatifs

2. Comparaison des différentes formes alléliques du gène
3. Mise en forme des séquences pour la suite du travail
Charger les fichiers d’allèles: “Fichier”, “Ouvrir”, edit7034.edi situé dans Anagene/Sauve, “OK”).
Puis, sélectionner toutes les séquences complètes du gène portant les préfixes Tyr (elles doivent apparaître sur
fond blanc). Garder le fichier “tyrcod1” en tête (il devient la référence de la comparaison).
Effectuer la comparaison (dans la barre d’outils: “Comparer les séquences” … “Comparaison
simple”.
En cas de doute pour un allèle, le sélectionner avec “tyrcod1” et recommencer la comparaison avec
l’option “Alignement avec discontinuité”.
Remplir le tableau suivant (selon le modèle proposé) afin de distinguer les différentes
formes alléliques (”tyrcod1” est choisi comme référence).
1
page 2
Séquence nucléique Polypeptide
Nom des
allèles Nucléotides changés
Nature - Position Triplets changés
Nature - Position Acides aminés changés
Nature - Position Type de mutation
tyrcod 1
tyrcod2
tyralba1
tyralba2
tyralba3
tyralba4
tyralba5
tyralbb1
tyralbts
référence référence référence référence
G 1147 Ù A
A 575 Ù C
A 575 Ù C
G 533 Ù A
A 575 Ù C
GT 731-732 Ù __
GAT 383 Ù AAT
TAT 192 Ù TCT
TAT 192 Ù TCT
TGG 178 Ù TAG (stop)
TAT 192 Ù TCT
TGT 244 Ù TGA (stop)
Asp 383 Ù Asn
Tyr 192 Ù Ser
Tyr 192 Ù Ser
Trp 178 Ù non-sens
Tyr 192 Ù Ser
Cys 244 Ù non-sens
substitution faux-sens
substitution faux-sens
substitution faux-sens
substitution non-sens en 178
substitution faux-sens
délétion, non-sens en 244
En utilisant l’outil “Comparaison” “Alignement avec discontinuité”, vérifier que toutes les
séquences ne portant pas le préfixe Tyr- sont celles du gène soigneusement débarrassé de ses extrémités
grâce aux enzymes Bsm I (reconnaissant GAATGC ou GCATTC) et Bgl II (reconnaissant AGATCT).
Présenter rapidement la méthode de vérification.
Une fois la vérification effectuée, construire le dernier allèle raccourci “albts” correspondant à
l’allèle entier “tyralbts”: “Fichier”, “Créer”, type ADN, nom albts, “OK”.
Copier sur la séquence Tyralbts la partie à conserver, puis la coller dans la ligne albts qui vient d’être
crée.
Eliminer toutes les séquences portant le préfixe Tyr- devenues inutiles: les sélectionner puis cliquer
sur l’icône “Supprimer” (croix).
A partir de cet instant, tout le travail portera sur les allèles raccourcis.
1

1Reporter, sur la représentation schématique ci-dessous, les sites de coupure ain-
si que les longueurs des différents fragments que l'on pourra ensuite tenter de séparer
par électrophorèse. Pour les longueurs, prendre le brin du haut comme référence.
0 200 400 600 800 1000 1200
“cod1”
“cod2”
Enzyme choisie: Sites de reconnaissance de l’enzyme:
4. Choix d'une enzyme de restriction susceptible de permettre l’identification des 2 allèles fonctionnels du gène page 3
Sélectionner les 2 allèles concernés (voir titre) et les comparer (voir précédemment).
Observer ce qui les distingue ainsi que les nucléotides les plus proches dans la chaîne.
Consulter la liste des enzymes de restriction disponibles (ci-contre). En choisir une qui
pourrait permettre de distinguer les 2 allèles. Faire agir cette enzyme sur les 2 allèles (barre
d’outils: icone “Action enzymatique” ..... “Représentation graphique” ..... “Fichier”, dans le
répertoire “Anagene/Sauve” ..... sélectionner “Tyrrest2.zym” .....ok ..... Dans la nouvelle fenêtre
“Carte de restriction”, sélectionner l’enzyme choisie précédemment et les 2 allèles étudiés grâce
aux menus déroulants.
Mnl I CCTC ou GAGG
Hae III GGCC
Hpa II CCGG
Alw I GGATC ou GATCC
Xba I TCTAGA
Einv IV AGTGTG
Enzymes
disponibles Sites de reconnaissance

Ouvrir le fichier “simul_electroph.xls” (ta-
bleur-grapheur) puis simuler les 2 électrophorèses des
fragments de restriction obtenus précédemment.
Dans la réalité, on devrait utiliser différents types
de gel d’électrophorèse: par exemple, un “gel 1” qui per-
met la séparation des fragments de taille moyenne (100 à
1000 kb) et un “gel 2” celle des petits fragments (10 à 100
kb). Pour la suite du travail, on supposera que l’on est
capable de réaliser:
Ice type d’électrophorèse
Iun “marquage” correct de l’ensemble des frag-
ments.
En s’aidant de la simulation précédente, placer
les différents fragments de restriction, obtenus pour les
2 allèles , sur les 4 bandelettes d’électrophorèse . Les re-
présenter par des barres noires transversales.
Indiquerlesensdemigrationdesfragments.
Quel est, dans le cas présenté, le gel le plus inté-
ressant à utiliser et quel est le fragment le plus intéres-
sant à repérer afin d’identifier clairement les 2 allèles
fonctionnels.
Echelle
approximative
du nombre
de bases des
fragments de
restriction
10 et moins
100 et plus
20
40
60
80
100 et moins
1000 et plus
200
600
800
400
4. suite … page 4
tyrcod1 tyrcod2
Avec l’enzyme
...............................
Gel 1
Gel 2
1
Témoins
de tailles (kb)
1500
750
500
250
120
150
60
30
15

Tableau du nombre de fragments d'ADN obtenus par restriction
1
1S’il dispose de ces enzymes, comment le biologiste peut-il s'y prendre pour mettre en
évidence la présence de la mutation “tyralbb1” ? de la mutation” tyralba4” ?
Les 6 enzymes sont-elles toutes indispensables pour la détection d’une éventuelle
anomalie du gène considéré? (c’est-à-dire peut-on se permettre d’en enlever une ?) Expliquer.
5. Détection des différentes formes du gène à l'aide
d'une batterie d'enzymes de restriction
cod 1
cod2
alba1
alba2
alba3
alba4
alba5
albb1
albts
Mnl I HaeIII Hpa II Alw I Xba I Einv IV
Enzymes disponibles
Allèles fonctionnels et autres versions mutées
page 5
Sélectionner les 9 fichiers d’allèles et faire agir les 6 enzymes du fichier “Tyrrest2.zym”.
Demander l’affichage sous forme de tableau et cliquer sur les différentes enzymes pour les activer .....ok
Compléter le tableau du nombre de fragments de restriction obtenus.
(Attention: le logiciel ne donne que le nombre de sites de coupure).
 6
6
1
/
6
100%