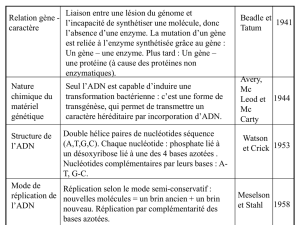
Outils enzymatiques en techniques de biologie moléculaire

Techniques en bio mol BH 04 Semestre 4
1
Techniques en biologie moléculaire
I. Introduction
Technique nécessaires dans toute la bio
Permet d’avoir une bonne connaissance du génome.
DNA
Transcription
rRNA mRNA tRNA
Ribosome
Traduction
Protéine
Techniques de plus en plus pointues. On verra les principales. Ces connaissances permettent un
progrès dans la recherche fondamentale, en bio et en médecine.
A. Recherche fondamentale
Composition et structure des génomes
Structure des gènes
Fonctionnement des gènes (régulation)
Fonction des gènes
B. Recherche appliquée
Biomédical
Production de molécules à intérêt
Thérapeutique
Forensique
Biotechnologies
II. Rappels simples
L’ADN est une molécule double brin, en hélice, maintenue par des liaisons hydrogènes. Elle a une
capacité de réplication semi conservative. Ceci produit 2 molécules identiques à la parentale. Cette
capacité de réplication est à la base de toutes les techniques de biologie moléculaire.
L’ARN est composé d’un seul brin, la plupart du temps, mais on peut le trouver sous la forme de
double brin.

Techniques en bio mol BH 04 Semestre 4
2
Schémas dessin de base des acides nucléiques et des 5 bases azotées.
La synthèse de l’ADN se fait toujours dans le sens 5’-3’.Toutes les polymérases fonctionnent dans ce
sens. Ne pas oublier d’indiquer la polarité des molécules quand on écrit une séquence d’ADN.
Schémas appariement de bases.
La distance entre 2 bases est de 0,34 nm. Il y a 10 paires de bases pour un pas d’hélice (hélice B).
330 Dalton = masse moléculaire d’un nucléotide.
660 Dalton = masse moléculaire d’une paire de bases.
Pas de A avec un C ou un T avec un G car il faut une taille bien spéciale pour l’hélice. Il faut donc une
base purique avec une base pyrimidique.
L’ADN est double brin, mais il peut être simple brin. Un ADN simple brin ou un ARN peut former des
structures spécifiques de façon locale, dans le cas ou deux séquences complémentaires se suivent, et
sont séparées par une partie qui ne s’apparie pas : Structure en tige-boucle.
Possibilité de circulariser la molécule. Ces molécules circulaires ont une structure particulière. En
effet, à cause des tensions, les molécules deviennent surenroulées. Un cercle circulaire ouvert est
possible si un des deux brins est coupé. Il existe donc 3 formes principales : forme linéaire, forme
circulaire surenroulée (fermée), forme circulaire relâchée (ouverte).
III. Les propriétés physicochimiques de l’ADN
A. La viscosité des solutions d’ADN
Elle n’a pas tellement d’intérêt pour l’étude fondamentale, mais elle a un intérêt pour la
manipulation. Les molécules d’ADN sont extrêmement visqueuses. L’ADN linéaire est plus visqueux
que l’ADN circulaire. L’absorption UV maximale est à 260 nm pour l’ADN, comme pour l’ARN. Pour
l’ADN double brin, la densité optique à 260 nm vaut 1, et donne 50 μg/mL pour une cuve de 1cm.
Pour l’ARN, la densité optique à 260 nm vaut 1, et donne 40 μg/mL. Si un ADN double brin devient
simple brin (qui se comporte comme un ARN), on le verra sur l’absorption.
B. Les charges de l’ADN
L’ADN fortement chargé, c’est un polyanion très chargé. Il est possible de faire de l’électrophorèse
sur un gel. La migration se sous l’effet d’un champ électrique de la cathode vers l’anode.
C. La dénaturation
La dénaturation, et la renaturation sont la deuxième grande propriété de l’ADN, à la base de toutes
les techniques. Si on chauffe une molécule d’ADN, on élimine les liaisons hydrogène, et donc l’ADN
double brin devient simple brin.

Techniques en bio mol BH 04 Semestre 4
3
Densité optique
Double brin séparation simple brin
20°C 90°C 100°C température
On détermine la température de fusion : T°m
La température de fusion T°m est une spécificité d’une molécule d’ADN donnée : plus la molécule est
longue, plus elle a de liaisons, et donc plus elle est stable, et plus elle est dure à dénaturer. Dans le
cas de 2 ADN identiques, plus un ADN est riche en GC, plus il va être stable. Des bases
complémentaires peuvent se renaturer, à condition de refroidir lentement. On peut définir
l’hybridation/renaturation, qui dépend aussi du nombre de liaisons hydrogènes. On peut déterminer
TH, qui est la température d’hybridation. C’est la température optimale de renaturation, à laquelle la
renaturation se fait le plus vite. Elle est inférieure de 15-20°C à T°m pour de longues molécules
(>100nt), et de 5°C pour des molécules de 20 nucléotides.
+ 5’ 3’
5’
5’ 5’ 5’ renaturation
5’ 3’ 3’ 5’
Dénaturation 3’ sonde
3’ 3’ 3’ 3’ hybridation 3’ 5’ 5’
3’ 5’
5’ 5’ 3’ 3’
Pour avoir de l’hybridation, le critère essentiel est la complémentarité. La concentration relative des
produits est le facteur favorisant la renaturation ou l’hybridation. L’hybridation permet de repérer les
appariements, grâce à la notion de sonde, en marquant la sonde avec un composé fluorescent, ou un

Techniques en bio mol BH 04 Semestre 4
4
marquage radioactif. On peut faire des hybrides ADN-ADN, mais aussi des ADN-ARN (stabilité +), et
ARN-ARN (stabilité ++).
D. Réplication
La réplication utilise la DNA polymérase, qui est capable de copier de l’ADN, et elles ont besoin
d’ADN matrice, ce sont donc des DNA polymérases DNA dépendantes. Il faut une amorce 3’OH pour
pouvoir commencer la réplication. Un ADN nu ne peut pas être la matrice de la synthèse d’un autre
brin. Il faut une amorce pour pouvoir commencer la réplication. C’est un oligonucléotide, une courte
séquence d’ADN qui a de la complémentarité avec l’ADN matrice. On peut donc hybrider par
complémentarité l’amorce sur la matrice. On a donc une séquence 3’OH libre, qui permet de
répliquer. Une DNA polymérase ne peut pas fonctionner s’il n’y a pas d’amorce. L’hybridation est liée
à la température. La température est donc le principal facteur de toutes les techniques de biologie
moléculaire.
A 99% les DNA polymérases sont DNA dépendantes. Il existe quelques cas particuliers.
E. Le gène
Région codante
ATG Stop
ORF
5’ 3’
3’ 5’
AUG Stop
5’ 3’
M
Brin transcrit brin non transcrit
= brin codant = brin non codant
= brin - =brin +
ORF = Open Reading Frame
AUG n’est jamais au début de l’ARN
1. Cadre de lecture
5’ ACGCCGACTACGCAT 3’
2. Clonage
Au sein d’une population d’ADN :
1. Repérer la séquence particulière (gène)
Promoteur

Techniques en bio mol BH 04 Semestre 4
5
2. Isoler le gène
3. Amplifier le gène : insérer le gène dans un vecteur (qui est capable de s’auto-répliquer)
IV. Méthodes d’analyse
A. Extraction d’acides nucléiques
Cellule/tissus phénol/chloroforme centrifugation
Phase aqueuse
Interphase
Phase organique
Le phénol dénature les protéines qui précipitent dans l’interphase. Le phénol et le chloroforme sont
assez toxiques. On peut faire un précipité dans le fond du tube en ajoutant 2 volumes d’éthanol, 150
mM de NaCl, pour un volume de mélange.
L’absorption à 260 nm et à 280 nm doit être mesurée, car les protéines absorbent à 280 nm. Ensuite,
il faut faire le rapport 260/280, qui vaut 2 pour un ADN pur.
B. Electrophorèse
Supports : gel d’agarose ou gel de polyacrylamide. L’électrophorèse permet d’évaluer la présence et
la taille de l’ADN : plus la taille est grande, plus la migration sera faible. La migration sur gel d’agarose
dépend de la structure, la plus rapide sera la molécule d’ADN circulaire ouverte, ensuite ce sera la
forme linéaire, et la plus lente sera la forme circulaire fermée. Pour de tout petits ADN ou ARN, la
vitesse dépend de la composition en bases. Le gel de polyacrylamide est utilisé pour le séquençage.
V. Outils enzymatiques en techniques de biologie moléculaire
A. Les enzymes de restriction
Elles coupent l’ADN double brin, et sont généralement inefficace sur l’ADN simple brin ou l’ARN. Elle
coupe en un site de restriction, spécifique de chaque enzyme. Ce sont des endonucléases. Les sites
de restriction sont en général de 4 à 6 paires de bases. Les sites de restriction sont en général des
palindromes. Fréquence de coupure par les enzymes de restriction. Les enzymes de restrictions sont
utilisées généralement pour le clonage. On coupe le génome en petits morceaux, et on se pose la
question de savoir la taille moyenne des morceaux.
Fréquence de coupure
5’ 3’ ¼ 4= 1/256
G A T C coupe enzyme de restriction ¼ 6= 1/4096
¼ ¼ ¼ ¼
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
1
/
23
100%