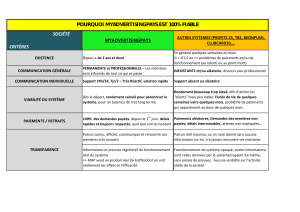
Vaches atteintes de paratuberculose


DÉVELOPPEMENT DE STRATÉGIES ET D’OUTILS
ANALYTIQUES NOVATEURS POUR LA DÉTECTION DE
VACHES ATTEINTES DE PARATUBERCULOSE
par
David Fock-Chow-Tho
Mémoire présenté au Département de biologie en vue
de l’obtention du grade de maître ès sciences (M. Sc.)
FACULTÉ DES SCIENCES
UNIVERSITÉ DE SHERBROOKE
Sherbrooke, Québec, Canada, 15 décembre 2016

Le 15 décembre 2016
Le jury a accepté le mémoire de Monsieur David Fock-Chow-Tho dans sa version finale.
Membres du jury
Professeure Nathalie Bissonnette
Directrice de recherche
Professeure associée au Département de biologie
Chercheur Scientifique d’Agriculture et Agroalimentaire Canada
Professeur Viktor Steimle
Codirecteur de recherche
Département de biologie
Professeur Nicolas Gevry
Évaluateur interne
Département de biologie
Professeur Richard Blouin
Président-rapporteur
Département de biologie

iv
SOMMAIRE
La paratuberculose bovine est une maladie causée par la mycobactérie Mycobacterium avium
subsp. paratuberculosis (MAP). Elle est responsable d’énormes pertes économiques dans le
monde. En effet, cette maladie provoque la diminution de la production laitière chez les
vaches ainsi qu’un état de fatigue général en raison d’une entérite chronique chez les sujets
atteints. Des indices mettent également en évidence le potentiel zoonotique de MAP et
malheureusement aucun traitement n’est connu à ce jour. Ainsi, les stratégies actuelles pour
contrer la maladie dans les troupeaux reposent plutôt sur des actions préventives.
Actuellement, le diagnostic de la paratuberculose reste difficile et la prévalence de la maladie
est probablement sous-estimée dans les troupeaux en raison de la faible sensibilité des tests
diagnostiques.
Dans l’optique de développer une nouvelle méthode diagnostique pour la paratuberculose, ce
projet de recherche s’est établi en deux étapes : la mise en place d’un système de diagnostic
robuste des animaux par les méthodes de dépistage traditionnelles, incluant une étude
comparative de l’efficacité de trousses commerciales, et finalement l’étude de la prolifération
cellulaire spécifique des lymphocytes comme d’une épreuve diagnostique pour la maladie.
Ainsi, la comparaison des trousses commerciales a démontré un écart d’efficacité qui a permis
d’établir de nouvelles recommandations pour l’analyse des animaux ainsi que l’amélioration
du diagnostic de la paratuberculose dans les troupeaux. Concernant le développement d’une
méthode de diagnostique basée sur la prolifération lymphocytaire, de nombreuses difficultés
techniques ont entravé le bon déroulement du projet mais ces travaux montrent la possibilité
de caractériser de manière plus complète les différents types lymphocytaires par cytométrie de
flux chez le bovin laitier.
Mots-clés : paratuberculose bovine, lymphocytes, prolifération, diagnostic

v
REMERCIEMENTS
J’aimerai tout d’abord remercier le Dre Nathalie Bissonnette pour l’opportunité qu’elle m’a
offert de travailler au sein de son équipe, ainsi que de m’avoir empêché de succomber à mon
premier vrai hiver.
Bien entendu, je remercie également ma conjointe Laura Segondy pour son support
inconditionnel et sa patience remarquable à mon égard.
Il en va de même pour ma famille que j’ai laissée loin derrière moi et sans qui aucune
aventure ne se serait jamais commencée.
Clin d’œil à Olivier Ariel qui fut mon guide culturel ainsi que mon complice au cours de ces
dernières années et qui restera, je l’espère, un bon ami.
Idem à Jean-Simon Brouard, arrivé un peu tard, mais qui m’a rappelé comment je faisais et
devais faire les choses.
Je suis reconnaissant aux membres de mon comité de conseillers d’avoir accepté de
m’encadrer, merci.
Et finalement, j’envoie mes pensées à tous les autres qui ont été là au cours de ces 3 ans,
humains ou animaux, autant pour le meilleur que pour le pire.
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
 24
24
 25
25
 26
26
 27
27
 28
28
 29
29
 30
30
 31
31
 32
32
 33
33
 34
34
 35
35
 36
36
 37
37
 38
38
 39
39
 40
40
 41
41
 42
42
 43
43
 44
44
 45
45
 46
46
 47
47
 48
48
 49
49
 50
50
 51
51
 52
52
 53
53
 54
54
 55
55
 56
56
 57
57
 58
58
 59
59
 60
60
 61
61
 62
62
 63
63
 64
64
 65
65
 66
66
 67
67
 68
68
 69
69
 70
70
 71
71
 72
72
 73
73
 74
74
 75
75
 76
76
 77
77
 78
78
 79
79
 80
80
 81
81
 82
82
 83
83
 84
84
 85
85
 86
86
 87
87
 88
88
 89
89
 90
90
 91
91
 92
92
 93
93
 94
94
 95
95
 96
96
 97
97
 98
98
 99
99
 100
100
 101
101
 102
102
 103
103
 104
104
 105
105
 106
106
 107
107
 108
108
 109
109
 110
110
 111
111
 112
112
 113
113
 114
114
 115
115
 116
116
 117
117
 118
118
 119
119
 120
120
 121
121
 122
122
 123
123
 124
124
 125
125
 126
126
 127
127
 128
128
 129
129
 130
130
1
/
130
100%