Formation Python du 14 Octobre 2010

Formation Python du 14 Octobre 2010
Version 1.0.1
Dimitri Bonnet, François Cuenot, Alexandre Vaudrey
12 October 2010


Table des matières
1 Organisation 3
1.1 Déroulement de la formation ..................................... 3
2 Préalables à la formation 5
2.1 Outils à installer avant la formation (linux) ............................. 5
2.2 Outils à installer avant la formation (windows) ........................... 5
3 Introduction à Python 7
3.1 Opérations de base .......................................... 7
3.2 Les variables ............................................. 7
3.3 Les blocs & sections de code ..................................... 8
3.4 Les types ............................................... 9
3.5 Définition de fonctions et passage de paramètres .......................... 10
3.6 Exemple de structure de contrôle .................................. 10
4 Numpy 13
4.1 Introduction à numpy ........................................ 13
4.2 L’indexing, le slicing et le broadcasting avec numpy ........................ 15
5 Matplotlib 19
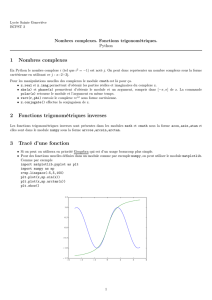
5.1 Tracé de courbes ........................................... 19
5.2 Tracé d’une fonction bidimensionnelle en courbes de niveaux ................... 21
6 Exemples 25
6.1 Exemples de traitement d’image ................................... 25
6.2 Résolution approchée d’équations non linéaires ........................... 31
6.3 Optimisation ............................................. 33
6.4 Equations différentielles ....................................... 38
7 Quelques liens... 43
Index 45
i

ii
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
 24
24
 25
25
 26
26
 27
27
 28
28
 29
29
 30
30
 31
31
 32
32
 33
33
 34
34
 35
35
 36
36
 37
37
 38
38
 39
39
 40
40
 41
41
 42
42
 43
43
 44
44
 45
45
 46
46
 47
47
 48
48
 49
49
 50
50
1
/
50
100%