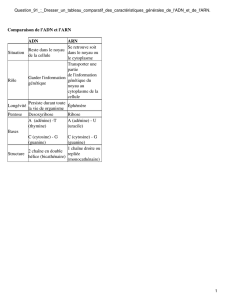
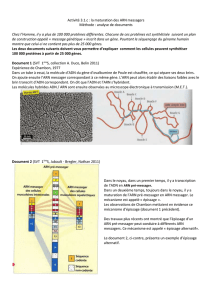
Résumé - LabUnix

François Major (Département d’Informatique et de Recherche Opérationnelle,
Université de Montréal)
Titre : Modéliser les petits et les grands ARN avec les outils MC-Fold et MC-Sym
Résumé : L'ère post cristallographique du ribosome et un enthousiasme récent
pour la régulation génétique par de petits ARN a grandement stimulé de manière
générale la recherche sur les ARN. En particulier, dans notre laboratoire, nous
avons développé des outils informatiques pour étudier systématiquement
l'architecture des structures tridimensionnelle (3D) d'ARN. À l'aide de ces outils,
nous avons identifié et formalisé un nouvel élément fondamental : le motif
cyclique de nucléotides (NCM) qui est plus général que l'élément classique utilisé
dans les algorithmes de prédiction de structures secondaires (2D). Pour savoir si
le NCM donne un avantage pour la prédiction et la modélisation, nous avons
développé un nouvel algorithme de prédiction de structures secondaires, MC-
Fold, et modifié notre algorithme de modélisation 3D, MC-Sym. Nous avons
ensuite montré les avantages d'utiliser le NCM aux niveaux 2D et 3D et
développé un pipeline qui permet de modéliser la structure 3D d'un ARN à partir
de sa séquence (1D) de nucléotides. Dans cette présentation, je vais montrer en
quoi le NCM est avantageux et comment on peut maintenant s'attaquer à la
modélisation 3D de petits mais aussi de grands ARN à l'aide de cette nouvelle
génération d'algorithmes.
1
/
1
100%