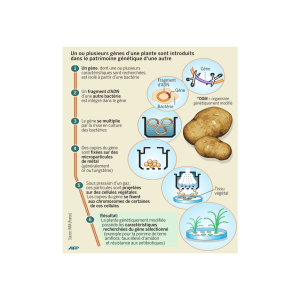
Assignment #2

Biologie Moléculaire-2013
Page 1 de 4
Devoir No6
Exercice 9
Contrôle transcriptionnel de Mel1 (Analyse northern)
1. Soumettre une figure de votre hybridation Northern avec une légende appropriée.
2. Obtenir les données densitométriques pour les ARN ribosomaux sur votre gel d’ARN
ainsi que les signaux d’ARN messagers obtenus aux différents temps suite au
transfère au galactose ou au glucose + galactose. Soumettre un tableau des données
brutes obtint avec imageJ pour le Northern et le gel d’ARN correspondent. Votre
tableau doit inclure les données brutes (les valeurs pour chacune des aires), les
valeurs normalisées (Mel1/rRNA) pour chacun des temps et l’expression relative aux
différents temps après le transfert comparativement au temps zero (Ex. Valeur
normalisée pour 1 heure/valeur normalisé temps 0).
Mutagénèse dirigé de LacZ : Essai de beta galactosidase
3. Soumettre un tableau des données et l’analyse correspondante des essais de beta
galactosidase. Votre tableau doit inclure :
a. Les absorbances moyennes et les DO600 pour chacun des mutants pour
chacune des dilutions testées.
b. Les unités d'activité calculée pour chacun des mutants.
c. Les activités relatives comparativement au témoin pUC.
d. Le type d’acide aminé substitué que chaque muant représente (Ex.
conservé, semiconservé, etc.)
e. Une légende qui indique quel mutant démontre la réduction relative
d’activité la plus élevée.
Contrôle traductionnel de Mel1
4. Soumettre un tableau des données et l’analyse correspondante des essais d’alpha
galactosidase. Votre tableau doit inclure :
a. Les absorbances et les DO600 pour chacune des dilutions de cultures
respectives obtenues pour les essais d’alpha galactosidase représentants les
différents temps suite au transfert au galactose ou au galactose + glucose.
b. Les unités d'activité calculée pour chacun des temps.
c. Les activités relatives comparativement au temps 0. Une légende qui
indique si les différences dans les activités observées sont conformes au
niveau de transcrit observé.

Biologie Moléculaire-2013
Page 2 de 4
Bio-informatique :
1. Soumettre la séquence annotée (nucléotide avec les acides aminés correspondants) de
l'ORF le plus long de la séquence virale1.
2. Est-ce que la séquence soumise dans la question précédente représente la séquence du
génome viral, de l'ARNm, ou les deux?
3. Soumettre l'information suivante sur l'ORF le plus long des séquences virale1 et
virale2:
La définition
L'organisme duquel le gène provient
Le nom du gène (pas du produit du gène)
Le nom du produit du gène
4. Soumettre l'information suivante pour la séquence virale3:
Quels SNPs (single nucleotide polymorphisms) est-ce que la séquence viral3 a
acquis?
Quel est le pourcentage d'identité nucléotidique entre les séquences viral1 et
viral3?
Quel est le pourcentage d'identité protéique entre les séquences viral1 et viral3?
Quel type de changements d'acides aminés sont survenus: conservé, semi-
conservé ou non conservé?
5. Parmi les SNP retrouvés dans la séquence virale3, est-ce que tous changent l'acide
aminé codé? Si non, donner un exemple spécifique où cela n'est pas le cas. Inclure le
codon original, le nouveau codon, et l'acide aminé correspondant dans les deux cas.
6. Quels trois domaines protéiques conservés sont présents dans la séquence humaine
inconnue?
Boni (2.5 points totaux sur ce devoir)
Vous devriez maintenant être assez familier avec le site de NCBI et être en mesure
de compléter l'exercice suivant avec peu de directives. Considérez ceci comme une
pratique pour la partie de bio-informatique qui sera sur l'examen final
GGCTCGCTGCCTCGCATTGCCACAGGCTCCTGAGAGGTCGCGGGCAGTGCCTGCGGGGA
GGCGCGGGGCCCTGCTCTGTAGGGCTGAAGGCCGCCCGAGGTTCGCCAAGGCTCTGGGC
TCTCGAAAGGAAGCCAAGAAAA
1. Cette séquence provient de quel gène?
2. Quel est le numéro d’accession de ce gène?
3. Cette séquence provient de quel organisme?
4. Quel est le numéro d’accession de cette protéine?
5. Donner le numéro d’accession d’un orthologue protéique de rat (Rattus Norvegicus).
6. Quel est le pourcentage d’identité protéique entre les protéines humaines et de rats.
7. Combien de fois est-ce que BamHI et HincII coupent dans le gène humain?

Biologie Moléculaire-2013
Page 3 de 4
8. Laquelle des amorces suivantes pourraient s'hybrider à l'ARNm du gène humain afin
de permettre une réaction de transcriptase inverse?
A. CAACCCATCACACAAAAC
B. GCATTGTAGCTTGTGTTGC
C. CTGACCGTTTTGTGTGATG
D. GCTTATTACGGTATCTCTG
9. La séquence sur la page suivante a été obtenue d'un patient. Possède-t-elle un ou
plusieurs SNP? Si oui quels sont-ils? Indiquer la position ainsi que le changement de
base. (Ex. G218 à C).
10. Est-ce que ces SNP changent le cadre de lecture du gène?

Biologie Moléculaire-2013
Page 4 de 4
ATGAGGACTCTGAACACCTCTGCCATGGACGGGACTGGGCTGGTGGTGGAGA
GGGACTTCTCTGTTCGTATCCTCACTGCCTGTTTCCTGTCGCTGCTCATCCTGT
CCACGCTCCTGGGGAACACGCTGGTCTGTGCTGCCGTTATCAGGTTCCGACAC
CTGCGGTCCAAGGTGACCAACTTCTTTGTCATCTCCTTGGCTGTGTCAGATCT
CTTGGTGGCCGTCCTGGTCATGCCCTGGAAGGCAGTGGCTGAGATTGCTGGCT
TCTGGCCCTTTGGGTCCTTCTGTAACATCTGGGTGGCCTTTGACATCATGTGCT
CCACTGCATCCATCCTCAACCTCTGTGTGATCAGCGTGGACAGGTATTGGGCT
ATCTCCAGCCCTTTCCGGTATGAGAGAAAGATGACCCCCAAGGCAGCCTTCA
TCCTGATCAGTGTGGCATGGACCTTGTCTGTACTCATCTCCTTCATCCCAGTG
CAGCTCAGCTGGCACAAGGCAAAACCCACAAGCCCCTCTGATGGAAATGCCA
CTTCCCTGGCTGAGACCATAGACGACTGTGACTCCAGCCTCAGCAGGACATA
TGCCATCTCATCCTCTGTAATAAGCTTTTACATCCCTGTGGCCATCATGATTGT
CACCTACACCAGGATCTACAGGATTGCTCAGAAACAAATACGGCGCATTGCG
GCCTTGGAGAGGGCAGCAGTCCACGCCAAGAATTGCCAGACCACCACAGGT
AATGGAAAGCCTGTCGAATGTTCTCAACCGGAAAGTTCTTTTAAGATGTCCTT
CAAAAGAGAAACTAAAGTCCTGAAGACTCTGTCGGTGATCATGGGTGTGTTT
GTGTGCTGTTGGCTACCTTTCTTCATCTTGAACTGCATTTTGCCCTTCTGTGGG
TCTGGGGAGACGCAGCCCTTCTGCATTGATTCCAACACCTTTGACGTGTTTGT
GTGGTTTGGGTGGGCTAATTCATCCTTGAACCCCATCATTTATGCCTTTAATG
CTGATTTTCGGAAGGCATTTTCAACCCTCTTAGGATGCTACAGACTTTGCCCT
GCGACGAATAATGCCATAGAGACGGTGAGTATCAATAACAATGGGGCCGCG
ATGTTTTCCAGCCATCATGAGCCACGAGGCTCCATCTCCAAGGAGTGCAATCT
GGTTTACCTGATCCCACATGCTGTGGGCTCCTCTGAGGACCTGAAAAAGGAG
GAGGCAGCTGGCATCGCCAGACCCTTGGAGAAGCTGTCCCCAGCCCTATCAG
TCATATTGGACTATGACACTGACGTCTCTCTGGAGAAGATCCAACCCATCACA
CAAAACGGTCAGCACCCAACCTGA
1
/
4
100%