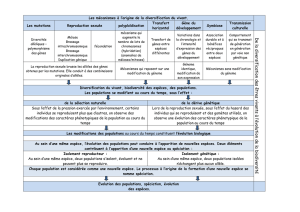
Biodiversité trans-spécifique chez la souris domestique

Biodiversité trans-spécifique chez la souris
domestique : une approche génomique.
Déposé le : 26 fevrier 2007
Date de début : 1 octobre 2007
Sujet susceptible d'obtenir une : Allocation Recherche
ANR blanche 2005 (jusqu’en déc 2008), et ANR Biodiversité 2006 (jusqu’en déc 2009)
couvrent les expériences mais pas l’allocation de thèse.
Directeur : Pierre BOURSOT
04 67 14 46 86 - 04 67 14 45 54 - [email protected]
Encadrement : Encadrement théorique par le directeur de thèse. A la paillasse par un
technicien dédié au projet. Collaboration avec un ingénieur informaticien programmeur.
Thématique : Recherche des déterminants historiques et sélectifs de la distribution de la
diversité génomique lors d’un processus de différenciation et de spéciation.
Détail : La biodiversité se crée dans les populations, se distribue dans leurs populations filles,
qui peuvent ensuite se différencier, puis échanger secondairement de la diversité. Cette
dynamique qui peut mener à la spéciation est pour partie aléatoire et sous contingence
historique, pour partie déterminée par l’effet de la sélection naturelle. Les patrons de
coalescence des gènes dans et entre les populations (ou espèces proches) peuvent être inférés
par l’étude des variations de séquences d’ADN et nous renseignent sur la part de ces deux
types de déterminants. Nous pouvons ainsi appréhender l’implication de la sélection naturelle
dans le maintien, la ségrégation ou les mélanges de la diversité au cours d’évènements de
spéciation. Sur un organisme modèle tel que la souris, l’approche peut être génomique, et
faire le lien avec les caractéristiques du génome (organisation, recombinaison), et les aspects
fonctionnels (fonction et expression des gènes).
Profil recherché: Formation en génétique des populations et évolution moléculaire, et/ou en
bioinformatique.
Domaine : Biodiversité, génétique des populations, évolution moléculaire, génomique.
Objectif : La Biodiversité Trans-Spécifique (BTS) est la composante de la biodiversité neutre
et fonctionnelle commune entre les espèces, c’est à dire le polymorphisme nucléotidique
qu’elles partagent. La BTS neutre est générée par le maintien du polymorphisme ancestral,
des mutations récurrentes indépendantes ou encore par l’introgression génétique. La BTS
fonctionnelle est le résultat des mêmes processus, auxquels se surajoute l’effet de la sélection
naturelle qui peut soit accroître la BTS dans le cas de sélection balancée et d’introgression
adaptative, ou au contraire la diminuer dans le cas de sélection diversifiante et d’adaptation
locale. La comparaison des patrons de BTS neutre et fonctionnelle entre régions génomiques
est un moyen d’identifier ce qui appartient à la biodiversité fonctionnelle.
Les sous-espèces de la souris domestique (Mus musculus) seront notre modèle pour aborder

ces questions. Nous exploiterons les données de re-séquençage et de typage de SNPs (Single
Nucleotide Polymorphisms) des bases de données pour identifier des régions génomiques
candidates pour la BTS ou au contraire la différenciation entre sous-espèces. Une approche
expérimentale par séquençage permettra ensuite d’améliorer les données sur les régions
candidates, en augmentant l’échantillonnage de génomes sauvages, qui est encore très limité
dans les bases de données.
L’étude comparative des patrons de coalescence des différentes régions du génome permettra
de tester des hypothèses relatives à l’influence de la sélection sur la détermination des patrons
de différenciation et de BTS entre les sous-espèces, et donc de quantifier l’influence de la
sélection sur la distribution de la biodiversité lors d’un processus de différenciation et un
début de spéciation, en relation avec les caractéristiques génomiques telles que la
recombinaison, la localisation chromosomique (chromosomes sexuels et autosomes) et les
caractéristiques fonctionnelles des gènes étudiés (lieux d’expression, fonction biochimique,
processus biologique, réseaux métaboliques).
Mots clés : Evolution moléculaire
Génétique des populations
Sélection
Coalescence
Spéciation
Génomique
Souris
Contexte : La vision de l’histoire des spéciations, et donc de la génération de la biodiversité,
sous forme d’un pattern de dichotomies successives a longtemps prévalu. Elle permet de
rendre compte de l’évolution à long terme et des relations entre les grands groupes
d’organismes. Toutefois le processus de spéciation implique des populations de génomes
complexes, dont les différentes composantes peuvent avoir des histoires indépendantes, et
subir des contraintes contrastées. Il est donc peu probable que ce pattern dichotomique simple
puisse rendre compte d’un tel processus complexe et multidimensionnel. C’est pourtant bien
dans cette complexité que peut être décrit et compris le processus de spéciation, c'est-à-dire
que peuvent être identifiées les forces évolutives et les contingences historiques qui
conduisent à la diversification du vivant.
Nombreuses sont les controverses sur les reconstitutions phylogénétiques d’espèces, en
fonction du gène étudié ou de la méthode employée. Dans le cas de taxons proches, de telles
controverses s’avèrent vaines puisqu’il y a plus de raisons théoriques d’attendre des
discordances que des concordances entre régions du génome. L’ADN mitochondrial a
longtemps été le marqueur de choix pour les comparaisons entre espèces proches. Toutes les
études récentes comparatives avec d’autres composantes du génome ont révélé des
discordances (pour ne citer que quelques exemples, Bachtrog et al. 2006; Ballard 2000;
Boissinot and Boursot 1997; Chan and Levin 2005; Melo-Ferreira et al. 2005; Pidancier et al.
2006). De même, les comparaisons entre régions du génome nucléaire montrent parfois des
contrastes très saisissants (par exemple Machado and Hey 2003; Pollard et al. 2006). L’étude
de telles discordances est elle-même très instructive, beaucoup plus que de tenter à tout prix
de réconcilier phylogénie des gènes et des espèces. Dans un nombre grandissant de cas,
l’étude de ces discordances fait sens et permet par exemple de pointer des gènes ou régions du
génome candidats pour l’acquisition de l’isolement reproductif, comme par exemple chez la
drosophile (Ting et al. 2000) ou plus récemment entre l’homme et le chimpanzé (Patterson et

al. 2006). De telles études stimulent les développements théoriques associés permettant
l’analyse de ces données complexes dans un cadre statistique de plus en plus rigoureux (Hey
2006; Hey and Nielsen 2004), visant à déterminer l’influence de la démographie, de la
sélection et des échanges secondaires dans la détermination de la ségrégation de la diversité
entre taxons proches.
La souris domestique (Mus musculus) est un excellent modèle pour aborder ces questions. En
effet, plusieurs sous-espèces différenciées occupant des aires de distribution disjointes sont
reconnues. Elles sont issues d’une radiation géographique à partir d’une zone de
différenciation initiale située au Moyen-Orient et au nord du sous-continent Indien, et
présentent des incompatibilités génétiques partielles, traduisant un début d’acquisition
d’isolement reproductif (Boursot et al. 1993). Les données préliminaires montrent des patrons
contrastés suivant les régions du génome, depuis un large partage de polymorphisme jusqu’à
une différenciation complète. La très bonne connaissance du génome de cette espèce permet
d’envisager une approche de cette question à l’échelle du génome, et de faire le lien entre les
patrons de différenciation observés, les propriétés locales du génome, et la fonction des gènes
concernés.
Méthode : Analyse bioinformatique : Les nombreuses données de polymorphisme déjà
disponibles pour la souris, sous forme de reséquençages de génomes complets, et de typage de
SNPs (Single Nucleotide Polymorphisms) à haut débit, sur des génomes de lignées de
laboratoire, et certains génomes d’origine sauvage des différentes sous-espèces, serviront à
définir des régions candidates pour des patrons de coalescence contrastés entre sous-espèces.
Les lignées de laboratoire étant des hybrides entre les sous-espèces, l’étude des déséquilibres
de liaison entre fractions du génome d’origines taxonomiques différentes servira également à
détecter les régions fonctionnellement différenciées participant à des incompatibilités entre
génomes.
Les gènes contenus dans ces régions candidates seront ensuite analysés à la lumière des bases
de données d’ontologie des gènes, d’expression différentielle dans différents organes et au
cours du développement, et d’implication dans des réseaux métaboliques. Ceci permettra
d’affiner et de rationaliser le choix de régions et gènes candidats.
Séquençage : Les gènes candidats retenus par l’analyse bioinformatique seront séquencés
dans un panel représentatif des sous-espèces de la souris domestique. L’échantillonnage est
disponible au laboratoire.
Analyse des données de séquence : Les données de séquence seront analysées en utilisant la
batterie de logiciels de génétique des populations et de simulations existante, ainsi qu’avec les
nouveaux outils statistiques développés par les partenaires du projet ANR, qui viseront plus
spécifiquement à faire la part entre les différentes causes possibles de TSB (persistance de
polymorphisme ancestral neutre ou sous sélection diversifiante, introgression secondaire).
Résultat attendu : L’analyse bioinformatique des données de polymorphisme à l’échelle
génomique permettra de tester les corrélations entre les patrons de polymorphisme et de
divergence et divers paramètres d’intérêt : nature des chromosomes (sexuels ou autosomes),
intensité de la recombinaison, fonctions biologiques et patrons d’expression des gènes.
L’acquisition de nouvelles séquences de régions candidates permettra de vérifier sur un
meilleur échantillonnage de génomes les prédictions de l’analyse génomique. Ces données
permettront de tester les hypothèses sélectives émises, et de documenter des cas où la
sélection pourrait expliquer la différenciation, ou au contraire le maintien de polymorphisme
ancestral, ou encore l’introgression secondaire entre les sous-espèces.

Référence biblio : Bachtrog, D., K. Thornton, A. Clark, and P. Andolfatto. 2006. Extensive
introgression of mitochondrial DNA relative to nuclear genes in the Drosophila yakuba
species group. Evolution 60:292-302.
Ballard, J. W. O. 2000. When one is not enough: Introgression of mitochondrial DNA in
Drosophila. Molecular Biology and Evolution 17:1126-1130.
Boissinot, S., and P. Boursot. 1997. Discordant phylogeographic patterns between the Y
chromosome and mitochondrial DNA in the house mouse: selection on the Y chromosome?
Genetics 146:1019-1033.
Boursot, P., J.-C. Auffray, J. Britton-Davidian, and F. Bonhomme. 1993. The evolution of
house mice. Annual Review of Ecology and Systematics 24:119-152.
Chan, K. M. A., and S. A. Levin. 2005. LEAKY PREZYGOTIC ISOLATION AND
POROUS GENOMES: RAPID INTROGRESSION OF MATERNALLY INHERITED DNA.
Evolution 59:720-729.
Hey, J. 2006. Recent advances in assessing gene flow between diverging populations and
species. Current Opinion in Genetics & Development 16:592-596.
Hey, J., and R. Nielsen. 2004. Multilocus Methods for Estimating Population Sizes, Migration
Rates and Divergence Time, With Applications to the Divergence of Drosophila
pseudoobscura and D. persimilis. Genetics 167:747-760.
Machado, C. A., and J. Hey. 2003. The causes of phylogenetic conflict in a classic Drosophila
species group. Proc R Soc Lond B Biol Sci 270:1193-202.
Melo-Ferreira, J., P. Boursot, F. Suchentrunk, N. Ferrand, and P. C. Alves. 2005. Invasion
from the cold past: extensive introgression of mountain hare (Lepus timidus) mitochondrial
DNA into three other hare species in northern Iberia. Molecular Ecology 14:2459-2464.
Patterson, N., D. J. Richter, S. Gnerre, E. S. Lander, and D. Reich. 2006. Genetic evidence for
complex speciation of humans and chimpanzees. Nature 441:1103-1108.
Pidancier, N., S. Jordan, G. Luikart, and P. Taberlet. 2006. Evolutionary history of the genus
Capra (Mammalia, Artiodactyla): Discordance between mitochondrial DNA and Y-
chromosome phylogenies. Molecular Phylogenetics and Evolution 40:739-749.
Pollard, D. A., V. N. Iyer, A. M. Moses, and M. B. Eisen. 2006. Widespread Discordance of
Gene Trees with Species Tree in Drosophila: Evidence for Incomplete Lineage Sorting. PLoS
Genetics 2:e173.
Ting, C. T., S. C. Tsaur, and C. I. Wu. 2000. The phylogeny of closely related species as
revealed by the genealogy of a speciation gene, Odysseus. Proceedings of the National
Academy of Sciences of the United States of America 97:5313-5316.
1
/
4
100%