1. services proposes 2. preparation des echantillons par le porteur

DOC-20
FICHE PRODUIT :
RE-SEQUENÇAGE DE REGIONS CIBLEES
Date de mise à jour :
28/08/2013
Plate-forme BIOPUCES et SEQUENCAGE
IGBMC – 1, rue Laurent FRIES –
67404 ILLKIRCH CEDEX- France
http://www-microarrays.u-strasbg.fr/
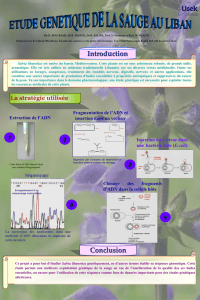
Le re-séquençage de régions ciblées combine des techniques d’enrichissement par capture
d’hybrides (SureSelect d’Agilent, …) et de séquençage haut débit. Il permet d’analyser, chez des
patients, des régions génomiques d’intérêt (exome, gènes cibles,…) afin d’y détecter des
variations génétiques par rapport à un génome de référence.
1. SERVICES PROPOSES
La plateforme réalise le séquençage des échantillons avec la technologie HiSeq2500 d’Illumina.
La prestation comprend :
1) Vérification des échantillons
Quantification de l’ADN génomique par spectrophotométrie (Nanodrop) ou fluorimétrie
(Qubit, Invitrogen)
Vérification de l’intégrité de l’ADN par électrophorèse
2) Préparation des librairies
Fragmentation de l’ADN par sonication (Covaris, KBiosciences)
Les fragments d’ADN sont ligués à des adaptateurs de séquençage possédant un index
(code barre de ≥ 6nt).
Vérification de la quantité de l’ADN fragmenté par fluorimètrie (Qubit) et du profil par
électrophorèse capillaire (Bioanalyzer, Agilent)
Capture des fragments d’ADN couvrant les régions d’intérêt du génome
Validation de la librairie par électrophorèse capillaire
3) Séquençage
Chargement des librairies sur la flowcell et génération de clusters avec la Cbot (Illumina)
Séquençage double 2x100 bases (paired-end)
4) Analyse primaire des données
Effectuée avec RTA/CASAVA (Illumina) : extraction des intensités des clusters à partir
des images, base calling, filtrage des séquences en fonction de leur qualité et suppression
des dimères d’adaptateur.
5) Analyse ultérieure (optionnelle)
2. PREPARATION DES ECHANTILLONS PAR LE PORTEUR DE PROJET
Le porteur de projet réalise la préparation de l’ADN génomique et nous le fournit pleine taille ou
fragmenté.
Caractéristiques de l’ADN à fournir
Quantité d’ADN
minimale requise
3 μg quantifiés avec un fluorimètre.
À une concentration ≥ 100 ng/μl dans un volume de 20 μl minimum.
Conditions d’envoi
En solution dans de l’eau sur de la carboglace.
Les tubes doivent être clairement identifiés et accompagnés d’une
fiche descriptive indiquant le volume de chaque ADN.
Nous ne commençons un run de séquençage que lorsque la Flowcell (8 pistes) est complète avec
des échantillons dont la longueur de lecture est similaire. Néanmoins, il nous est possible de
réaliser des runs rapides sur une seule piste de la flowcell moyennant un surcoût.
3. CONTROLES QUALITÉ RÉALISÉS PAR LA PLATEFORME
Les contrôles qualité listés ci-dessous, sont effectués par la plateforme et les résultats sont
envoyés par e-mail au porteur de projet à l’issue de chacune des étapes.

DOC-20
FICHE PRODUIT :
RE-SEQUENÇAGE DE REGIONS CIBLEES
Date de mise à jour :
28/08/2013
Plate-forme BIOPUCES et SEQUENCAGE
IGBMC – 1, rue Laurent FRIES –
67404 ILLKIRCH CEDEX- France
http://www-microarrays.u-strasbg.fr/
1) Vérification des échantillons
Quantité d’ADN génomique (mesurée au
fluorimètre)
≥ 3μg
Qualité
DO260/DO280 ≥ 1,8
- ADN génomique pleine taille : absence de signe
de dégradation sur un gel d’agarose
- ADN fragmenté : taille moyenne ≤ 500 pb
Les images de l’ADN avant fragmentation sont
demandées
2) Préparation des librairies
Profil de la librairie
(électrophorèse capillaire)
Pic(s) compris entre 200 et 800pb.
Pureté de la librairie
(électrophorèse capillaire)
Présence minoritaire de dimères d’adaptateur
(bande à 120-130pb)
3) Séquençage et analyse primaire des données
Moyenne des scores de qualité (Phred
score). Les moyennes sont calculées pour
chaque position (~base) sur l’ensemble
des séquences*.
≥ 30 pour 95% des positions
Nombre total de séquences* par
échantillon
≥ 75 millions**
* passant le filtre qualité et ne correspondant pas à des dimères d’adaptateur
** pour un échantillon séquencé sur une piste entière. Pour le reséquençage d’exome humain
nous multiplexons généralement deux échantillons par piste permettant d’obtenir une
couverture nucléotidique moyenne supérieure à 40X dans les régions capturées.
4. LIVRAISON DES RESULTATS
Pour chaque échantillon les résultats suivants sont mis à la disposition du porteur du projet :
- données brutes de séquençage (contient les séquences nucléotidiques au format
fastq ayant passé le filtre qualité et ne correspondant pas à des dimères
d’adaptateur).
Le porteur de projet peut télécharger ses données de séquence sur le serveur FTP de la
plateforme. Un login et un mot de passe sont attribués par la plateforme et envoyé par courriel.
Conformément aux « Conditions Générales de la Plate-forme Biopuces et Séquençage », il est
rappelé que le porteur du projet est responsable de la sauvegarde et de l’archivage de ses
données. La plateforme ne s’engage à les conserver que pour une durée limitée de 6 mois après leur
mise à disposition.
5. ANALYSE ULTERIEURE [OPTIONNEL]
L’analyse ultérieure des données n’est pas prise en charge dans la prestation standard, mais elle
peut être réalisée sous la forme d’une collaboration avec des membres de la plateforme. Elle
comprend notamment l’alignement des séquences sur le génome de référence, l’évaluation de
l’efficacité de la capture, la recherche de variants (variation ponctuelle (Single Nucleotide
Variant, SNV), petites insertions, délétions). La localisation des variants par rapport aux
annotations fonctionnelles du génome sont données (ex : 3’UTR, exon etc…) de même que leur
impact (synonyme, non-synonyme, codon stop, variant d’épissage…). Les variants détectés sont

DOC-20
FICHE PRODUIT :
RE-SEQUENÇAGE DE REGIONS CIBLEES
Date de mise à jour :
28/08/2013
Plate-forme BIOPUCES et SEQUENCAGE
IGBMC – 1, rue Laurent FRIES –
67404 ILLKIRCH CEDEX- France
http://www-microarrays.u-strasbg.fr/
également annotés avec des banques de données publiques comme dbSNP. Les variants de
plusieurs individus peuvent être comparés entre eux. Une analyse permettant la détection des
remaniements chromosomiques peut également être réalisée.
1
/
3
100%