Étude du profil des populations cellulaires du sang en vue d`une

Étude du profil des populations cellulaires du sang en
vue d’une application au diagnostic du lupus
érythémateux disséminé
Mémoire
Jennifer Lemieux
Maîtrise en microbiologie
Maître ès sciences (M.Sc.)
Québec, Canada
© Jennifer Lemieux, 2016

Étude du profil des populations cellulaires du sang en
vue d’une application au diagnostic du lupus
érythémateux disséminé
Mémoire
Jennifer Lemieux
Sous la direction de :
André Darveau, directeur de recherche
Sonia Néron, codirectrice de recherche

iii
Résumé
Le lupus érythémateux disséminé (LED) est une maladie auto-immune systémique dont le
diagnostic est très complexe. Le clinicien doit baser son diagnostic sur une liste de 11 critères
reliés à des observations cliniques et à des mesures sérologiques. Afin de faciliter ce diagnostic,
plusieurs groupes recherchent de nouveaux marqueurs biologiques quantifiables. C’est dans ce
but que la cytométrie en flux a été utilisée afin de comparer les cellules du sang des patients et
celles de sujets sains. La caractérisation exhaustive des sous-populations cellulaires montre que
l’expression de HLA-DR est amplifiée chez les patients même si la maladie est inactive. De plus,
l’analyse du contenu sérique en cytokines inflammatoires a montré que la quantité de GM-CSF
était plus importante chez les patients LED. Nos travaux suggèrent que HLA-DR et GM-CSF
pourraient être considérés comme des candidats intéressants dans les études sur le diagnostic du
LED.

iv
Table des matières
Résumé ........................................................................................................................................... iii
Table des matières ........................................................................................................................... iv
Liste des tableaux .......................................................................................................................... vii
Liste des figures ........................................................................................................................... viii
Liste des abréviations ...................................................................................................................... ix
Avant-propos ................................................................................................................................... xi
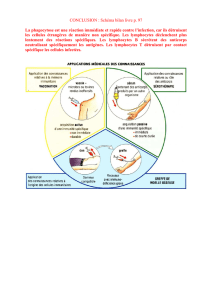
1. Introduction .................................................................................................................................. 1
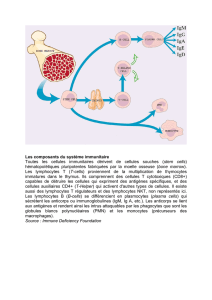
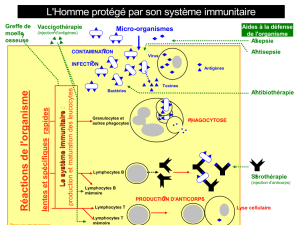
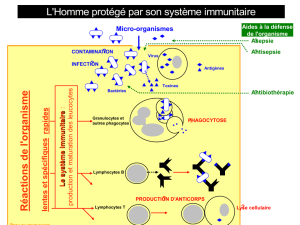
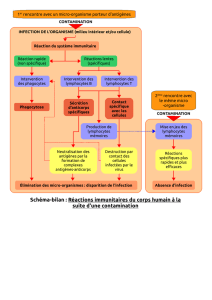
1.1 Immunité ................................................................................................................................. 1
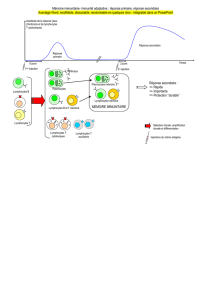
1.1.1 Réponse immunitaire et intermédiaires cellulaires .......................................................... 1
1.1.1.1 Réponse immunitaire innée ....................................................................................... 1
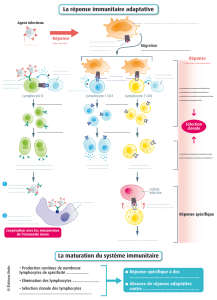
1.1.1.2 Réponse immunitaire adaptative ............................................................................... 2
1.1.2 Les lymphocytes B .......................................................................................................... 3
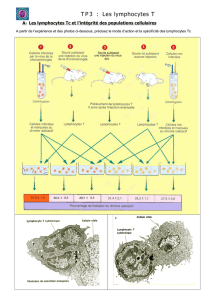
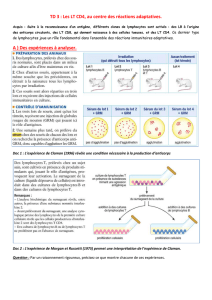
1.1.3 Les lymphocytes T ........................................................................................................... 4
1.1.4 Messagers ......................................................................................................................... 5
1.2 Lupus érythémateux disséminé .............................................................................................. 6
1.2.1 Causes .............................................................................................................................. 6
1.2.2 Diagnostic ........................................................................................................................ 7
1.2.3 Évaluation thérapeutique ................................................................................................. 8
1.2.4 Traitements .................................................................................................................... 11
1.2.5 Cellules impliquées dans la pathogénèse ....................................................................... 11
1.2.5.1 Modèles de souris .................................................................................................... 11
1.2.5.2 Lymphocytes T ........................................................................................................ 12
1.2.5.3 Lymphocytes B ....................................................................................................... 13
1.2.6 Cytokines ....................................................................................................................... 14
1.2.6.1 IL-6 .......................................................................................................................... 14
1.2.6.2 IL-10 ........................................................................................................................ 14
1.2.6.3 IL-17 ........................................................................................................................ 14
1.2.6.4 Interférons ............................................................................................................... 15
1.2.6.5 B-cell-activating factor ............................................................................................ 15

v
1.3 Cytométrie en flux et usage clinique .................................................................................... 16
1.3.1 Human Immunophenotyping Consortium ..................................................................... 16
1.3.2 Outils d’analyses de données multiparamétriques ......................................................... 18
1.3.2.1 SPADE et viSNE ..................................................................................................... 18
2. Hypothèse ................................................................................................................................... 19
3. Objectifs ..................................................................................................................................... 20
4. Méthodologie ............................................................................................................................. 21
4.1 Source des cellules mononucléées du sang, du sérum et du plasma .................................... 21
4.1.1 Participants en santé ....................................................................................................... 21
4.1.2 Patients LED .................................................................................................................. 22
4.2 Analyses phénotypiques ....................................................................................................... 23
4.2.1 Marquage extracellulaire ............................................................................................... 23
4.2.2 Anticorps ........................................................................................................................ 23
4.2.3 Acquisition et analyse des données ................................................................................ 26
4.2.3.1 Spanning-tree Progression Analysis of Density-normalized Events (SPADE) ...... 27
4.3 Dosage des facteurs solubles ................................................................................................ 28
4.3.1 ELISArray ...................................................................................................................... 28
4.3.2 Essai Bioplex ................................................................................................................. 28
4.4 Activation in vitro ................................................................................................................. 29
4.4.1 Milieu de culture ............................................................................................................ 29
4.4.2 Essais d’activation ......................................................................................................... 29
4.4.3 Mesure des facteurs solubles dans les surnageants de culture ....................................... 30
4.5 Analyses statistiques ............................................................................................................. 30
5. Résultats ..................................................................................................................................... 32
5.1 Caractéristiques médicales des patients et des participants à l’étude ................................... 32
5.2 Patron des cytokines ............................................................................................................. 35
5.2.1 Facteurs solubles dans le sérum des patients LED ........................................................ 37
5.2.3 Sécrétion in vitro ............................................................................................................ 43
5.3 Étude comparative de l’effet de la congélation sur les PBMC ............................................. 45
5.3.1 Effets de la congélation sur les lymphocytes et les monocytes ..................................... 45
5.3.2 Effets de la congélation sur les sous-populations des lymphocytes T ........................... 47
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
 24
24
 25
25
 26
26
 27
27
 28
28
 29
29
 30
30
 31
31
 32
32
 33
33
 34
34
 35
35
 36
36
 37
37
 38
38
 39
39
 40
40
 41
41
 42
42
 43
43
 44
44
 45
45
 46
46
 47
47
 48
48
 49
49
 50
50
 51
51
 52
52
 53
53
 54
54
 55
55
 56
56
 57
57
 58
58
 59
59
 60
60
 61
61
 62
62
 63
63
 64
64
 65
65
 66
66
 67
67
 68
68
 69
69
 70
70
 71
71
 72
72
 73
73
 74
74
 75
75
 76
76
 77
77
 78
78
 79
79
 80
80
 81
81
 82
82
 83
83
 84
84
 85
85
 86
86
 87
87
 88
88
 89
89
 90
90
 91
91
 92
92
 93
93
 94
94
 95
95
 96
96
 97
97
 98
98
 99
99
 100
100
 101
101
 102
102
 103
103
 104
104
 105
105
 106
106
 107
107
1
/
107
100%