Microscopie 3D

!"#!"
$%& %" %" $%& '(!%
$%")*+%'"+!!%"%%"%&
$#"%"#&"%"'%#$%! ")
,-./
(Coronarographie: 0# %" #" %&
!"#" %#& % %#% # %
1#"!+#"%!! "1#$%&%%2"3
#24%!#%!%%1#)
(Microscopie 3D: % 1#% %& " !! 5
+"&%%%"#"")0#%"
#" "# %& 67copy 2D – paste 3D78 # %
"%'" % #" "& $%9 +"#)
%& % %#% # 673D deconvolution microscopy
challenge78$International Symposium on Biomedical Imaging:
;<=5>cf.!(!"?)%%#>"#%"#"%&
!"#"%#&'%##"41#1#
$%++%"! % !% $%""%& % "
#"")
(Tomographie dynamique: 0# %" ! ! !"#
!"#5@%!"&% 1#)
/##! ! #"'5#"+%")
.A! #" 4 +" # !# !" #" "#
&#%%"%(>"#%""%'
!"#++!"#"'5@%&+%'"'
!""'de facto#!&"%)
(Réponse impulsionnelle variable: " !! 5 #
%&&%"! %## 2!%$%">
% " #"" " # # B !" !
"%%" % %"%") 0# %" #" 4
"#""""%""%%%%#9+"%:+9'
!"? % & :%C % #
!"#!" %?) 0# " %" $# #"
%! 67%#&78#%#(%"""4)
(Données multi-variées:%$!!%""
% #%"! % "" #(% :%(
# %(!%? $#" +%D" &'% "" % %"!
#!%""%")
!) '%#E#"(2"=)+
MiTiV7FMéthodes Inverses de
Traitement en Imagerie du Vivant
000,G
&%";<<H
%&'#
%&!"#
"%#&
Déconvolution aveugle en coronarographie
"+%! &% 1# # %1# "
%& !"#"%#&)0&%"
1#%"+"%#!"
#'#:#%%"#24!%!#%?)
&! # +"!"" " # # ""
:&%& %#%1#? % #" 1#"! I<
%&";"#)
best 3D deconvolution
algorithm (ISBI 2013)
best 3D deconvolution
algorithm (ISBI 2013)
Algorithme «Copy 2D – Paste 3D» de
déconvolution en microscopie 3D
"# %& !"#" # %
!!5$%###!#'
%%" :9>2? # % % #"
"&#"% :" C?) $%& " #%
" %& # "" # # 675
!"#" !!2 %"&78
""%"%2#"!%%&"&:
;<=5?)
FJJKKK)'!%%&"&)&J;<=5J&%J'(! %"&J
""'# !"#"5
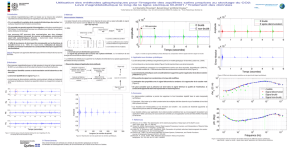
Reconstruction en tomographie dynamique
!"#!"2"%1#:9>2>C>?$#"!2!%
% "" %") # $%!1#" =;<
# L5< !") !"#!" =5 "%
: " M< !" % "%"? %"
!"%" # #") &#%%"
%( :N? 2 %& %! %"
')
#! ""7F " " %) !%"" O%
2"&2"%)
Déconvolution aveugle en microscopie 3D
!"#!"*#"'2""%)&%"
%1# %! +# ) / :'#
NPP"? %1# ! %" "2%#>
: MN;"? %1# +%"
!#'# Q5 :#& LMN"? %1#
%&&%"!#")
#! ""7F .++% et al. :;<=< " .)))
%&"& R !!2?7S !! 2#
:'!+ # T=<<> =)N 0/? LP;TP=;T=<N 9
LN)MTLN)MT;<<"U)
""'# !"#"
%#&5
FJJ)#"(2"=)+
# "" "%# 4 % :&% % %2" 3>
!! 5> 1#"! !"%&% 1#> "" %"1#
2!%? "# %" " %%"%& $%!
" # 9% $"+%" +%D" % " "%" "
!%%#24#%!+%#)
#$%&!%:&% %%2"3!"%&% ?>
" #% "" 1# # %& #" B
!"# % $#" "' # # J# %
# "'""1#%)% %#%!"#"
# %&"! % %# $"%& "# %
%%"%#%")
0 #% " !"#" %#& #" 1# $%#(%""%&
:B " 5? #" ! "1# +%' 1# # "" #
#%1#$%!#""#"" 1###)
/0//
=) " ! ! / 21# 2" :/*? R "#
$/ 21#%:/?7S
;) %'% -#' #" :-?> %'% ! "1#
$"&" !% % 9 V "+%1#>
% %1#/!%"."':J/.?
5) %OK%7S
N) "#"G#%":G?-W%%9#)
:X?!"%#
1
/
1
100%