Étude des classes d`atomes des protéines pour la prédiction d

Présenté par Mathieu Almeida, Amine Ghozlane
Analyses de Données Biologiques
05 février 2008
Rantanen V.V., Gyllenberg M., Koski T. et Johnson M.S.
Mars 2002 –Bioinformatics
Étude des classes d’atomes des protéines pour la
prédiction d’interactions moléculaires

Introduction
•Interactions moléculaires des protéines
–Nombreuses cibles possibles
•Ions, petites molécules, protéines, ADN, ARN
–Conception d’un médicament
Prédiction du ligandIdentification du ligand
•Criblage virtuel
Docking
•RMN
•Cristallographie
Rayon x

Introduction
•Interactions moléculaires des protéines
–Nombreuses cibles possibles
•Ions, petites molécules, protéines, ADN, ARN
–Conception d’un médicament
Prédiction du ligandIdentification du ligand
•Criblage virtuel
Docking
•RMN
•Cristallographie
Rayon x
On a besoin de comprendre comment s’effectue la liaison

•Identification des interactions
Introduction
Modélisation
Moléculaire Reconnaissance
statistique des
modèles
Analyse d’une
base de donnée
Identification des interactions
Évaluation des champs
de force
(GRID, AQUARIUS)
Évaluation statistique des
liaisons d’un groupement
(SuperStar, X-Site) Utilisation de
classes
d’atomes
Amélioration des classifications des atomes intervenant dans les
interactions protéiques

Construction d’une librairie d’interaction
12880 fichiers de coordonnées
Interaction protéine -ligand 930 pairs d’interaction protéine
–protéine non homologues
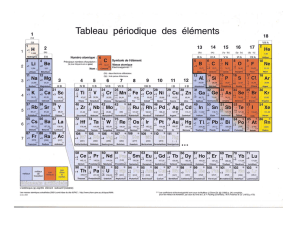
Classification en 24 classes des atomes des protéines impliqués
dans ces liaisons
Atomes impliqués dans les interactions
Li A.J. et
Nussinov R. 1998
Classes comportant
les même types
d’atomes
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
1
/
22
100%