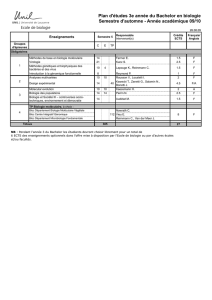
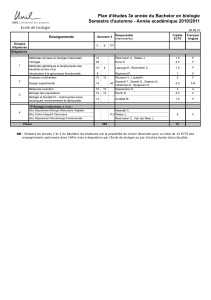
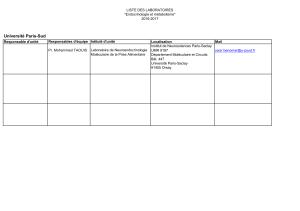
Dynamique moléculaire - Réseau Français de Chimie Théorique

Dynamique moléculaire
Outline
Introduction
Objectifs – méthode
Historique
Principe de la dynamique moléculaire
Séquence de mise en pratique
Comment obtenir le potentiel ?
Les formalismes
Formalisme de Newton
Formalisme de Lagrange
Formalisme de Hamilton
Les algorithmes de propagation
Le propagateur de Verlet
Le propagateur Velocity-Verlet
Les dynamiques moléculaires ab initio
Dynamique de Ehrenfest
Dynamique Born-Oppenheimer
Dynamique moléculaire Car-Parrinello

Dynamique moléculaire
Introduction
Objectifs – méthode
Objectifs et méthode
1. Calculer des moyennes statistiques d’un système à l’équilibre
2. Idem Monte Carlo
3. Principe ergodique :
hA(r(t),p(t))itime =hA(r,p)iensemble (1)
4. Echantillonner l’espace des phases
5. Technique “temporelle" d’échantillonnage plutôt qu’aléatoire comme en
MC
6. Evolution dans le temps du système
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
 24
24
 25
25
 26
26
 27
27
1
/
27
100%