COURS DE BIOLOGIE MOLÉCULAIRE
Présenté par:
Pr A.HAMMOUMI
Ecole supérieure de Technologie
1

BIOLOGIE MOLÉCULAIRE
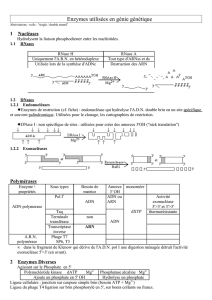
C’est une discipline consacrée à l'étude: des molécules qui portent
l’information génétique (=réplicons), leur structure, synthèse et altérations
(mutations).
L’information génétique est constituée des gènes codant pour des
protéines, mais également de séquences d'ADN non codantes, intervenant
dans la régulation de l'expression génique.
2
L’unité de l’information génétique est le gène.
La totalité de l’information génétique est le génome.

Le stockage du matériel génétique se fait dans une structure physiquement et
chimiquement stable. Cette structure doit être capable d’autoréplication et
d’autoréparation = réplicon
Les réplicons peuvent être :
l’ADN ou l’ARN chromosomique
ou l’ADN ou l’ARN extrachromosomique (plasmide, phage).
Pour la majorité des êtres vivants, cette structure est la double hélice formée de deux
brins antiparallèles (Watson et Crick, 1950).
I- L’INFORMATION GÉNÉTIQUE
3

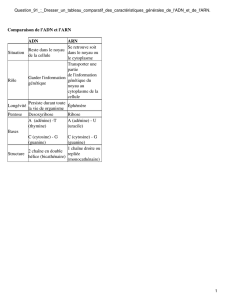
Les molécules d’acides nucléiques sont porteuses de l’information génétique.
Il en existe deux types:
ADN = acide désoxyribonucléique
ARN= acide ribonucléique
ADN: chaque cellule présente une copie du matériel génétique sous forme d’une
longue molécule d’ADN qui porte plusieurs milliers de gènes. Chaque gène est un
segment linéaire de la molécule d’ADN.
ARN: les molécules d'ARN sont beaucoup plus courtes, sont utilisées pour
transmettre l'information génétique à la machinerie cellulaire, et transporter un seul
ou quelques gènes.
4

Remarque: certains virus utilisent l'ARN pour coder leurs génomes. Ces virus à ARN
ont des génomes courts comportant une dizaine de gènes.
5
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
 24
24
 25
25
 26
26
 27
27
 28
28
 29
29
 30
30
 31
31
 32
32
 33
33
 34
34
 35
35
 36
36
 37
37
 38
38
 39
39
 40
40
 41
41
 42
42
 43
43
 44
44
 45
45
 46
46
 47
47
 48
48
 49
49
 50
50
 51
51
 52
52
 53
53
 54
54
 55
55
 56
56
 57
57
 58
58
 59
59
 60
60
 61
61
 62
62
 63
63
 64
64
 65
65
 66
66
 67
67
1
/
67
100%






![86 [Quels sont les constituants de l`ADN et de l`ARN? ] ADN](http://s1.studylibfr.com/store/data/007383263_1-9a41736365764fe43d1f9e7462bcdc21-300x300.png)