La réplication

1
Travaux dirigés de
Biologie Moléculaire
3

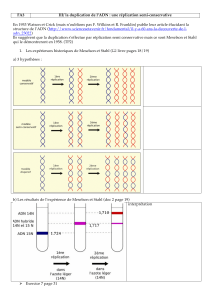
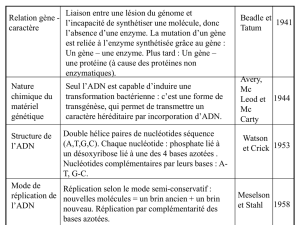
Expérience préliminaire, Meselson et Stahl, 1958
2

3 modèles de réplication
réplication
conservative réplication
dispersive réplication
semi-conservative
3

3 générations
ADN parental
ADN fils :
1ère génération
ADN fils :
2nde génération
4

5
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
 24
24
 25
25
 26
26
 27
27
 28
28
1
/
28
100%