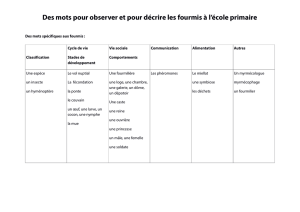
Vous avez dit espèces

Biologie moléculaire/bioinformatique
Microbiologie
Ecologie/biologie de l’insecte
Métabolomique
Chimie analytique
Métabarcoding
Chimie pharmacologique

Choix et pertinence du modèle: interactions biologiques – fourmis/bactérie
Vous avez dit espèces ?
G × G × E
S. R. Bordenstien et al., PLoS Biol, 2015, 13, e1002226.
C. R. Woese & N. Goldenfed, Microbiol. Mol. Biol. Rev., 2009, 73, 14.

C. Moreau et al., Science, 2006, 312, 101. N. Pierce et al., Molecular ecology, 2012, 21, 2282.
Choix et pertinence du modèle: interactions biologiques – fourmis/bactérie
Diversité des fourmis et des bactéries digestives associées

N. Pierce et al., PNAS, 2009, 106, 21236.
Impact des bactéries digestives sur l’évolution des fourmis arboricoles

J. Clardy et al., Nature,
1999, 701.
J. Clardy et al., Nature
Chem. Bio., 2009, 391.
attines cultivar (Basidomycètes)
Pseudonocardia
(actinobactéries) Pseudonocardia
Escovopsis
Fourmis attines et actinobactéries cuticulaires
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
 24
24
 25
25
 26
26
 27
27
1
/
27
100%