– UE : –VII I) Nutrition

2016-2017 Physiologie bactérienne
Biologie des Procaryotes et des Virus
– UE : –VII
Transcription
Pas d'annexes
Semaine : n°10 (du 07/11/16 au
11/11/16
Date : 09/09/2016
Heure : de 8h00-
9h00 Professeur : Pr. Romond
Binôme : n°34 Correcteur : n°5
Remarques du professeur : pas de remarque
PLAN DU COURS
Cours précèdent : On a fini la réplication d'ADN avec les deux systèmes unidirectionnels qui concernent plutôt les
chromosomes et le système diplasmique, c'est a dire en cercle roulant. Par ailleurs, on avait envisagé la
réplication rapide, c'est à dire, qu'on avait une réplication se met en marche avant même que nous avions fini de
faire deux nouveaux corps microbiates.
1/12
TYPE DE PLAN DE COURS :
I) Nutrition :
II) Croissance :
III) Métabolisme :
A) Réplication
B) Transcription
1) ARNm :

2016-2017 Physiologie bactérienne
I) Métabolisme :
A) Transcription :
Cette transcription ne va pas être du tout régulé comme est régulé le système eucaryote.
Parlons du système intron-exon : On aura pas de régulation possible par des zones qui ne sont pas transcrites. Tout
va être transcrits, effectivement, en dehors d'une partie des zones promotrices. Et c'est à ce niveau là que l'on va
voir une grande partie des régulations.
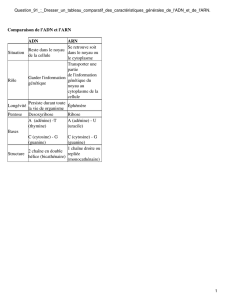
De façon comparable aux eucaryotes, on a va trouver un ARN avec ses bases qui vont être :
–Uracile
–Cytosine
–Guanine
–Adénine
=> Il nous manque la Thymine puisqu'elle va être remplacée par l'Uracile.
Pour l'instant, en terme d'acides nucléiques, nous sommes sur les mêmes schémas que l'on connait :
➔On a 3 ARN dans une cellule microbienne même si on a pas de membrane nucléaire. Donc c'est 3 ARN
vont se retrouver en particulier pour l'ARN ribosomal (ARNr) à des concentrations variables dans la
cellule en fonction des besoins en traduction :
➢ARN messager (ARNm)
➢ARN de transfert (ARNt)
➢ARNr
1) ARN messager :
Architecture :
C'est à ce niveau que va se trouver les zones permettant la régulation de la transcription. On verra que la
transcription une fois qu'elle déclenche est associé à la traduction.
Premier schémas :
2/12

2016-2017 Physiologie bactérienne
On se retrouve avec un énorme polypeptide après avoir fait un énorme ARNm avec plusieurs protéines qui sont
synthétisées en même temps.
Il va falloir contrôler l'énergie qu'on met à disposition pour éviter que l'on consomme trop d'énergie.
En avant de cette énorme séquence polypeptide, on va trouver une séquence de tête qui sera donc traduite
(correspond à 25-150 bases) et qui sont en partie 5'. (= Séquence de tête au niveau de l'ARNm qui va être
transcrite)
On a ensuite l'ARN codant pour le polypeptide et on a en extrémité 3' une séquence de queue qui elle même ne
sera pas traduite. (on a la transcription mais dans cette énorme structure d'ARNm, deux structures qui ne sera pas
traduites)
Si on part de notre ADN et qu'on a la structure double brin (on a le 5' → 3')
Le 3' va servir de brin matrice puisqu'on va avoir un brin d'ARNm qui lui même sera de 5' vers 3'.
Dans cette zone on va se trouver avec une première partie, qui va correspondre à la zone promoteur, qui elle même
n'est pas transcrite.
Ensuite on à la séquence de tête et donc c'est la séquence complémentaire.
Ensuite on arrive à cette séquence qui va correspondre à l'ensemble du polypeptide, qui sera donc traduit au
moment où on enclenche le système. Et on a donc notre séquence de queue (=séquence de pause). Et donc on
trouve la séquence complémentaire à ce niveau.
Une fois qu'on à l'architecture, comment se met en place le système de détection du démarrage de la
transcription ?
Système de détection de démarrage de la transcription :
Il faut un signal qui se trouve en amont de chaque polypeptide à transcrire et qui soit relativement homogène, qui
sont les bactéries.
Ce qu'in va parler concerne E.Coli (mais pas universel pour l'ensemble des bactéries) :
Sur l'ADN :
En -1 sur la zone promoteur on a le site de liaison de l'ARN polymérase.
En -35, on avait 6 bases qui sont relativement homogènes avec de la répétition donc on a le site de
reconnaissance au niveau du coté 5'. Et c'est à ce niveau là, que l'on va avoir un travail d'induction ou de
répression.
Il faut pour réguler une transcription, empêcher ou la favoriser. Il faut donc bien jouer sur le site de reconnaissance
de liaison de l'ARN polymérase.
Sur ce site de liaison qui va être important :
➔La boite de Pribnow : On va retrouver une séquence TATAAT qui est célèbre. C'est une zone qui est
consensus pour une fois chez les procaryotes. Ca permet quand on va faire une séquence d'ADN eucaryote
de sur le site de liaison TATAAT, par rapport à un ARN, d'anticiper sur a probabilité d'une zone
polypeptide.
3/12

2016-2017 Physiologie bactérienne
Sur l'ARN :
Séquence consensus de Shine-Dalgano (5'-AGGA-3'). Elle se situe dans cette séquence de tête.
On a ensuite un codon d'initiation (=AUG)
D'un point de vu structure, une première zone qui permet d'activer la transcription. Une fois que la transcription,
débute, on a un morceau d'ARN qui va commencer à être synthétisé.
Quand on arrive sur la synthèse de cette structure, on initie la traduction. Donc à peine que l'on ait démarré les
premiers codons, après le codon d'initiation, que l'on aura une traduction qui va se mettre en jeu. D'où dans
l'environnement de la zone transcrite, le besoin d'avoir les ARNt et les ARNr.
Une fois qu'on a cette structure, comment va se mettre en place ce système ?
On a besoin :
–d'un ARN polymérase dans l'environnement direct de ce brin qu'on a commencé à transcrire.
–Il faut les ATP, GTP, EDP et les CTP de façon à pouvoir commencer à faire la transcription, à partir du
brin matrice.
–Ensuite, il va falloir également, de l'ARNr puisqu'une fois qu'on débute notre ARNm, on va avoir besoin
de traduire tout de suite.
Donc ça nous donne un système, où si on imagine un ADN super enroulé, on va zoomer partiellement la zone à
transcrire pour pouvoir positionner notre ARN polymérase.
Donc on a compris que c'est ici que s'est passé, avec la zone de liaison, le démarrage et la boîte TATAAT. Et si on
imagine que notre polymérase s'était ajouté ici, on s trouve avec ensuite le début du brin. Donc la polymérase
continue d'avancer..
On va pouvoir avoir un système qui explique que l'on aura une partie N-terminale et C-terminale qui vont indiquer
quel est le sens de transcription. Et par déduction, pouvoir, sur un ARNm remonter à un ADN complémentaire (=
c'est ce qu'on fait lorsqu'on fait un séquençage à partir de l'ARN)
Donc il faut bien à un moment donné qu'on arrête, puisqu'on a vue qu'on avait déclenché le système par la
reconnaissance de la liaison. Il a fallu avoir eu une légère ouverture pour pouvoir avoir le positionnement de cet
ARN. Et donc à un moment donné faudra s'arrêter. Et donc on à la séquence complémentaire de la séquence de
pause de l'ARN.
4/12

2016-2017 Physiologie bactérienne
Comment va se mettre en place le système ?
Arrêt de l'ARN polymérase :
La séquence terminatrice va coder pour un ARN qui lui même va être de séquence répétée mais complémentaire,
de façon de pouvoir créer une épingle à cheveu. Ca va permettre sur cette zone là, on a une (proton??) ou un
entré très vite dès qu'on a démarré la synthèse de l'ARN sur cette partie là et bien on va avoir une boucle en état
gazeux qui va se créer naturellement.
Cette structure va jouer l'attachement de la polymérase (durée : milliseconde). Cette encombrement sur le brin
d'ARN va ralentir d'abord l'ARN polymérase. Il faut, pour obtenir l'arrêt total, des éléments complémentaires : Il y
a deux possibilités :
•Premier mécanisme : Derrière cette épingle à cheveu, il y a un code qui va permettre d'obtenir sur l'ARNt 6
uridines. Ces 6 uridines devraient permettre l'arrêt complet de l'ARN polymérase. (cas des bactéries).
Lorsqu'on va vouloir récupérer les ARNm, comme l'uridine est complémentaire de l'Adénine sur le brin
d'ADN, il suffit de chercher les zones poly-A pour savoir où on s'arrête.
Lorsqu'on veut le faire à partir d'une cellule eucaryote, une recherche des ARNm, on fait de la
transcription inverse. Donc on obtient l'ADN complémentaire. Et donc on va pouvoir accrocher les Poly-
A, donc on a la queue poly-A qui permet de dire qu'en amont on avait de l'ARN.
•Deuxième mécanisme : C'est la présence de protéine particulière : le facteur Rho qui suit la polymérase
qui au moment de la création sur l'ARN de cette épingle à cheveu, va venir taper la polymérase. C'est un
accident d'embouteillage et donc on la polymérase qui est arrêtée.
Une fois qu'on a cela, on se dit qu'on va pouvoir rentrer en transcription et derrière la traduction, sauf que comme
on a un polypeptide qui peut correspondre à 4-5 (ou plus) protéines : On appelle cela, cluster de gènes qui vont
être transcrits et traduits en même temps. Cela consomme de l'énergie.
Les bactéries qui sont les plus capables de gérer leur énergie et celles qui vont avoir un avantage écologique.
(population qui s'adapte)
=> On a une variabilité qui est toujours possible.
5/12
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
1
/
12
100%