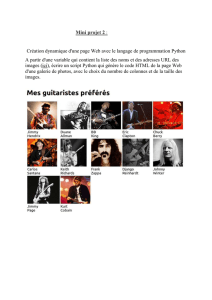
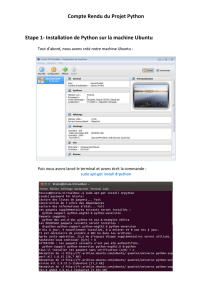
Support - Groupe Calcul

PYTHON
Pour le
calcul Scientifique
Konrad HINSEN
Centre de Biophysique Moléculaire (Orléans)
et
Synchrotron Soleil (St Aubin)

Une brève historique
1991: Python est publié
1994: premières applications scientifiques
1996: Numerical Python
.
.
.
2006:! - un grand choix de bibliothèques
!! - colloque annuel SciPy
!! - premier livre épuisé au bout de deux mois
!! - enseigné à plusieurs universités
!! - des entreprises spécialisés
!! - une formation du CNRS attire la foule

Quelques applications
Astronomie
ASTROLIB
et PyFITS
(Space Telescope
Science Institute)
Bioinformatique
BioPython
(Collaboration internationale)
Systèmes dynamiques
SimPy
(Collaboration
internationale)
Mathématiques
SAGE
(University of
Washington)
Statistique
Modular toolkit for
Data Processing
(Humboldt-
Universität)
Neurologie
Vision Egg
(Collaboration
internationale)
Eléments finis
FiPy
(NIST)
Géographie
Thuban
(Intevation
GmbH)
Visualisation
MayaVi
(Prabhu
Ramachandran)

Pourquoi Python ?
▹!Travail interactif
□!Développement rapide
□!Développement incrémentiel
□!Test, débogage
□!Analyse interactif de données

Pourquoi Python ?
▹!Travail interactif
▹!Simplicité du langage
□!Syntaxe claire et nette
□!Gestion automatique de la mémoire
□!Tout est dynamique,
!il n’y a rien à déclarer
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
1
/
22
100%