La traduction - L`UNF3S en 2015, c`est

Chapitre 6 :
La traduction
Professeur Joël LUNARDI
Année universitaire 2011/2012
Université Joseph Fourier de Grenoble - Tous droits réservés.
UE1 : Biochimie – Biologie moléculaire

Plan
I. Le code génétique
II. Les molécules informationnelles de la traduction
III. La traduction
Chapitre 6. La traduction

La traduction
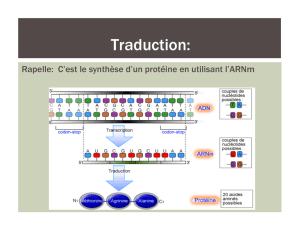
---GTGCACCTGACTCCTGAG---
---CACGTGGACTGAGGACTC---
--- GUGCACCUGACUCCUGAG ---
--val-his-leu-thr-pro-glu---

I. Le code génétique
1. Mise en évidence
- 4 bases vs 20 acides aminés
lecture des bases 1 à 1 : 41= 4 combinaisons
lecture des bases 2 à 2 : 42= 16 combinaisons
lecture des bases 3 à 3 : 43= 64 combinaisons
-mise en évidence expérimentale avec des polynucléotides de
synthèse et des systèmes de traduction in vitro
motif élémentaire de lecture : le codon formé par 3 nucléotides
I. Le code génétique

I. Le code génétique
UCAG
UU
UC
UA
UG
CU
CC
CA
CG
AU
AC
AA
AG
GU
GC
GA
GG
2ème position
1ère position (5 ’) 3ème position (3 ’)
2. Propriétés
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
 24
24
 25
25
 26
26
 27
27
 28
28
 29
29
 30
30
 31
31
 32
32
 33
33
 34
34
 35
35
 36
36
 37
37
 38
38
 39
39
 40
40
 41
41
 42
42
 43
43
 44
44
1
/
44
100%




![6. La synthèse des protéines [biologie cellulaire]](http://s1.studylibfr.com/store/data/002655458_1-7f252533d141d9bd8de010a3541ba2bb-300x300.png)