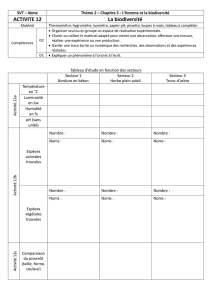
Cours 1

Organisation des assemblages d'espèces dans les guildes écologiques
Olivier Hardy (Université Libre de Bruxelles; ohar[email protected])
-> background: génétique des populations
intérêt pour l’écologie des communautés car analogie des mécanismes
Plan:
Organisation des communautés: visions d’hier et d’aujourd’hui
Introduction au modèle neutre de Hubbell
Organisation spatiale des communautés en condition “quasi”-neutre
Divergence phylogénétique/fonctionnelle et assemblage d’espèces
Test de structure phylogénétique/fonctionnelle – problèmes des modèles nuls

0%
1%
2%
3%
4%
5%
6%
7%
8%
9%
10%
0
500
1000
1500
2000
2500
3000
3500
4000
1980
1981
1982
1983
1984
1985
1986
1987
1988
1989
1990
1991
1992
1993
1994
1995
1996
1997
1998
1999
2000
2001
2002
2003
2004
2005
2006
2007
2008
2009
2010
2011
2012
Number of articles with 'ecolog*' AND 'communit*' (title, abstract, keywords)
% articles including also 'phylogen*'
% articles including also 'neutral*'
Données tirées de la base de données Scopus pour le sous-ensemble de >4300 revues
scientifiques classées dans « Life Sciences ».

Parallélisme des processus de structuration au sein des populations
(diversité génétique) et des communautés (diversité spécifique)
Génétique des populations
distribution des allèles
au sein d’une espèce
Ecologie des communautés
distribution des espèces
au sein d’une communauté
- mutation
- dispersion (migration)
- dérive génétique
- sélection
- spéciation
- dispersion (migration)
- dérive écologique (démographique)
- adaptation / interactions écol.
modèles
neutralistes
Processus Processus

Communautés végétales :
visions d'hier et d'aujourd'hui
Quels processus organisent les communautés végétales?
Facteurs déterministes
-> vision « classique »
Facteurs stochastiques
-> modèles neutralistes
Intégration écologie – évolution – biogéographie
-> structure phylogénétique des communautés

Quels facteurs organisent les communautés végétales?
Vision classique : les espèces se distribuent en
fonction des gradients environnementaux
 6
6
 7
7
 8
8
 9
9
 10
10
 11
11
 12
12
 13
13
 14
14
 15
15
 16
16
 17
17
 18
18
 19
19
 20
20
 21
21
 22
22
 23
23
 24
24
 25
25
 26
26
 27
27
 28
28
 29
29
 30
30
 31
31
 32
32
 33
33
 34
34
 35
35
 36
36
 37
37
 38
38
 39
39
 40
40
 41
41
 42
42
 43
43
 44
44
 45
45
 46
46
 47
47
 48
48
 49
49
 50
50
 51
51
 52
52
 53
53
 54
54
 55
55
 56
56
 57
57
 58
58
 59
59
 60
60
 61
61
 62
62
1
/
62
100%