Nicolas Girard – Ingénieur Chercheur en Bioinformatique

Nicolas Girard
Ingénieur Chercheur en Bioinformatique
Détails personnel
Né le 12 avril 1991, 24 ans
Adresse 22 rue Basse, 30200 Codolet, France
Téléphone +33 (0)6 7486 3737
Mail nicolas.gira[email protected]
Linkedin se.linkedin.com/in/NiGirard
Diplômes
2013–2015 Master en Bioinformatique
,Université des Sciences et Techniques, Nantes,
France.
Formation pluridisciplinaire : Biologie, Statistique et Informatique. Compétence en géné-
tique, épigénétique, séquençage de seconde génération (NGS) et biochimie structurale.
Compétences liées à l’informatique : algorithmes (network et machine-learning), base de
données et programmation objet.
2012–2013 Licence générale en Biologie, Biochimie et Physiologie annimale
,Université
des Sciences et Techniques, Nantes, France.
Connaissances avancées en Biologie moléculaire, biochimie, virologie, bactériologie ainsi
qu’en physiologie et immunologie humaine. Culture cellulaire et expérimentation animale
pratiquée.
2011–2012 DEUG en Biologie et Biochimie
,Université des Sciences et Techniques, Nantes,
France.
Connaissances en biologie cellulaire, annimale et végétale. Apprentissage de concepts chim-
iques et biochimiques. Techniques aquises : PCR, test Elisa, chromatographie, microscopie,
centrifugation, western blot.
Expérience
2015–
En cours
CDD
,Ingénieur Chercheur, Site nuclaire de Marcoule, DSV. Bagnols-sur-Cèze,
France.
Activité d’ingénieur d’étude et de développement dans le cadre du programme interministériel
de R&D, confié au CEA, pour lutter contre les menaces terroristes NRBC sur le territoire
(nucléaire, radiologique, biologique et chimique). Amélioration d’applications existantes,
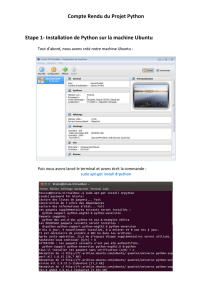
preuves de concept, ainsi qu’optimisation d’algorithmes effectués avec le langage Python
sous un environnement Windows.

2015
6 mois
Stage
,Étudiant en Master, Université Polytechnique de Chalmers à Götenborg,
Suède.
Modélisation d’un réseau métabolique pour une bactérie impliquée dans le cancer Colorectale
:Fusobacterium nucleatum, sous la direction de Jens Nielsen. Développement d’algorithmes
ayant pour objectif d’aider à la résolution de réseaux complexes avec le langage Python sous
environnement Linux.
2014
2 mois
Stage,Étudiant en Master, Faculté de Médecine, Marseille, France.
Création de paramètres statistiques pour le contrôle-qualité sur des fichiers de sorties issus
de NGS (Technologie Illumina). Conceptualisation et développement en Python d’un logiciel
dédié à cette tache : RunE.
2013
1 mois
Stage,Étudiant, Nantes, France.
Stage volontaire. Travail sur des cellules souches et analyse de radiolographie dans le cadre
de la recherche d’un traitement contre la Myopathie de Duchenne. Écriture de protocoles
et culture de cellules souches.
Langues
Français Langue Maternelle
Anglais Professionnel 6 mois en Suède
Langages informatiques utilisés
Principaux Python, SQL, C, Bash
Secondaires CSS, Java, C++, HTML, R,
LateX, PHP, Javascript, Matlab
Intérêts
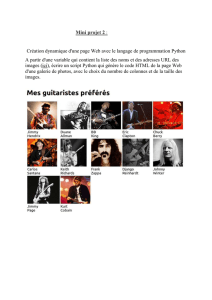
Aïkido Combats à mains nues et armés : Jo, Bokken et Tanto
Musique Violoniste débutant, écoute tous genre de musique
Cinéma Sci-fi, thriller
Références
Boyang JI, superviseur stage 2015
Position Post-Doc, Chercheur en Bioinformatique
Organisation Chalmers University of Technology
Adresse Kemivägen 10, SE-412 96 Göteborg, Sweden
Mail boy[email protected]
Olivier CROCE, superviseur stage 2014
Position Ingénieur Chercheur en Bioinformatique
Organisation IHU Marseille, CNRS
Adresse 27, boulevard Jean Moulin, 13385 Marseille Cedex 5, France
Mail olivier.cro[email protected]
1
/
2
100%