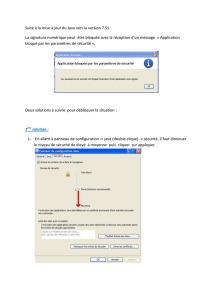
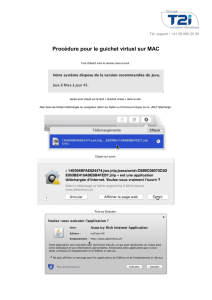
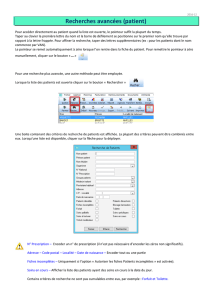
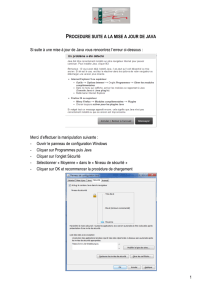
Terminale S Fiche Méthode #4 – Utiliser le logiciel - TheoSVT

Terminale S
Fiche Méthode #4 – Utiliser le logiciel Phylogène
Les autres fiches méthodes utilisées en classe sont disponibles sur le site http://theosvt.free.fr bsavoye2007
OBJECTIF
Le logiciel Phylogène permet de construire des arbres
phylogénétiques à partir de caractères ou de molécules.
CONSTRUIRE (UNE MATRICE DE CARACTERES)
Choisir une collection (ex. Vertébrés-Lycée’).
Cliquer sur ‘Construire’.
Sélectionner les espèces en cliquant sur chacune d’elles.
Un nouveau clic sur la figure enlève l’espèce de la
sélection. Choisir les caractères dans le menu déroulant.
Indiquer dans le tableau les états des caractères, en
cliquant dans chacune des cases et en utilisant les
informations qui apparaissent en bas, à droite de l’écran.
Vérifier votre tableau. Corriger si nécessaire. Exemple :
POLARISER (ET CODER LES CARACTERES)
Choisir le taxon extra-groupe (espèce qui présente tous les
caractères à l’état primitif).
Colorer les états primitifs, puis les états dérivés avec une
autre couleur. Déplacer éventuellement les colonnes et les
lignes pour regrouper les niveaux entre eux.
ÉTABLIR DES PARENTES
Cliquer sur ‘Établir des parentés’. Passer en mode édition
(Choix|Éditer l’arbre, puis )
Cliquer sur les différentes espèces pour faire apparaître les
taxons dans l’arbre.
Relier deux taxons qui possèdent un caractère au même
niveau (dérivé par ex.) par un trait.
A partir du bouton ‘Choix’, il est possible d’afficher les
boîtes de l’arbre (taxons)
Il est possible de nommer les taxons en cliquant sur
chaque nœud (une liste de groupes apparaît alors).
Faire ‘Choix|afficher les noms de groupe’ pour les afficher
sur l’arbre.
COMPARAISONS MOLECULAIRES
Après avoir choisi une collection, faire,
‘Fichier|Ouvrir|Tableau de séquences’.
Sélectionner les espèces (bouton enfoncé) dont on veut
comparer les séquences (indiquées par une lettre pour
chaque acide aminé)
Cliquer sur pour afficher l’arbre
phylogénétique correspondant.
Il est possible de modifier le mode d’affichage de l’arbre
dans .
La permet de comparer le nombre de
différences entre les différentes séquences, soit comptées
en nombre d’acides aminés, soit en pourcentage (à définir
dans ).
Les distances peuvent être affichées sur l’arbre à l’aide du
bouton .
LES OUTILS POUR LA CONSTRUCTION D’UN ARBRE
PHYLOGENETIQUE
Annule les opérations réalisées (une par une).
Zoom avant et zoom arrière
Mode édition. Permet de réarranger les branches de
l’arbre et l’affichage du code couleur.
Permutation des branches autour d’un nœud. Cliquer sur
cette icône puis se placer au niveau d’un nœud et cliquer
à nouveau.
Annule toutes les opérations. Retour au point de départ
(origine commune à tous les taxons)
Affiche sur l’arbre phylogénétique moléculaire les
distances (soit en acides aminés, soit en pourcentage)
1
/
1
100%